ผู้ใช้:M sky/วิวัฒนาการ
| ส่วนหนึ่งของบทความทางชีววิทยาชุด |
| วิวัฒนาการ |
|---|
 |
| กลไกและกระบวนการ |
| ประวัติและงานวิจัย |
| วิวัฒนาการทางชีววิทยา |
ในด้านชีววิทยา วิวัฒนาการ (อังกฤษ: Evolution) คือการเปลี่ยนแปลงทางพันธุกรรมในประชากรของสิ่งมีชีวิต จากรุ่นหนึ่งสู่รุ่นหนึ่ง วิวัฒนาการเกิดจากกระบวนการหลัก 3 กระบวนการ ได้แก่ ความแปรผัน การสืบพันธุ์ และการคัดเลือก โดยอาศัยยีนเป็นตัวกลางในการส่งผ่านลักษณะทางพันธุกรรม อันเป็นพื้นฐานของการเกิดวิวัฒนาการ ลักษณะเช่นนี้เกิดขึ้นในประชากรเพื่อให้เกิดความแปรผันทางพันธุกรรมเมื่อสิ่งมีชีวิตให้กำเนิดลูกหลานย่อมเกิดลักษณะใหม่ หรือเปลี่ยนแปลงลักษณะเดิม โดยลักษณะใหม่ที่เกิดขึ้นนี้มีสาเหตุสำคัญ 2 ประการ ประการหนึ่ง เกิดจากกระบวนการกลายพันธุ์ของยีน และอีกประการหนึ่ง เกิดจากการแลกเปลี่ยนยีนระหว่างประชากร และระหว่างสปีชีส์ ในสิ่งมีชีวิตที่มีการสืบพันธุ์แบบอาศัยเพศ สิ่งมีชีวิตใหม่ที่เกิดขึ้นจะผ่านกระบวนการแลกเปลี่ยนยีน อันก่อให้เกิดความแปรผันทางพันธุกรรมที่หลากหลายในสิ่งมีชีวิต วิวัฒนาการเกิดขึ้นเมื่อความแตกต่างทางพันธุกรรมเกิดขึ้น จนเกิดความแตกต่างมากขึ้นเรื่อยๆ จนกลายเป็นลักษณะที่แตกต่างกัน
กลไกในการเกิดวิวัฒนาการแบ่งได้ 2 กลไก กลไกหนึ่งคือการคัดเลือกโดยธรรมชาติ (natural selection) อันเป็นกระบวนการคัดเลือกสิ่งมีชีวิตที่มีลักษณะเหมาะสมที่จะอยู่รอด และสืบพันธุ์จนได้ลักษณะที่เหมาะสมที่สุด และลักษณะที่ไม่เหมาะสมจะเหลือน้อยลง กลไกนี้เกิดขึ้นเพื่อคัดเลือกลักษณะของประชากรที่เกิดประโยชน์ในการสืบพันธุ์สูงสุด[1][2] เมื่อสิ่งมีชีวิตหลายรุ่นได้ผ่านพ้นไป ก็จะเกิดกระบวนการปรับตัวของสิ่งมีชีวิต เพื่อให้อยู่ในสิ่งแวดล้อมได้อย่างเหมาะสม[3]
กลไกที่สองในการขับเคลื่อนกระบวนการวิวัฒนาการคือการแปรผันทางพันธุกรรม (genetic drift) อันเป็นกระบวนการอิสระจากการคัดเลือกความถี่ของยีนประชากรแบบสุ่ม การแปรผันทางพันธุกรรมเป็นผลมาจากการอยู่รอด และการสืบพันธุ์ของสิ่งมีชีวิต แม้ว่าการแปรผันทางพันธุกรรมในแต่ละรุ่นนั้นจะเปลี่ยนแปลงเพียงเล็กน้อย แต่ลักษณะเหล่านี้จะสะสมจากรุ่นสู่รุ่น เกิดการเปลี่ยนแปลงทีละเล็กละน้อยในสิ่งมีชีวิต จนกระทั่งเวลาผ่านไปเป็นระยะเวลานาน จะทำให้เกิดการเปลี่ยนแปลงขึ้นในลักษณะของสิ่งมีชีวิต กระบวนการดังกล่าวเมื่อถึงจุดสูงสุดจะทำให้กำเนิดสปีชีส์ชนิดใหม่[4] แม้กระนั้น ความคล้ายคลึงกันระหว่างสิ่งมีชีวิตมีข้อเสนอที่เป็นที่รู้จักกันดีคือการสืบเชื้อสายจากบรรพบุรุษ (หรือยีนพูลของบรรพบุรุษ) เมื่อผ่านกระบวนการนี้จะก่อให้เกิดความหลากหลายมากขึ้นทีละเล็กละน้อย[1]
เอกสารหลักฐานทางชีววิทยาวิวัฒนาการชี้ให้เห็นว่ากระบวนการวิวิฒนาการเป็นสิ่งที่เกิดขึ้นจริง ทฤษฎีอยู่ในช่วงของการทดลอง และพัฒนาในสาเหตดังกล่าว การศึกษาซากฟอสซิล และความหลากหลายทางชีวภาพของสิ่งมีชีวิตทำให้นักวิทยาศาสตร์ช่วงกลางคริสศตวรรษที่ 19 ส่วนใหญ่เชื่อว่าสปีชีส์มีการเปลี่ยนแปลงมาตลอดในระยะเวลาที่ผ่านมา[5][6] อย่างไรก็ตาม กระบวนการที่ขับเคลื่อนการเปลี่ยนแปลงนี้เป็นปริศนาต่อนักวิทยาศาสตร์ทั่วไป จนกระทั่งปี พ.ศ. 2402 ชาร์ล ดาวิน ตีพิมพ์หนังสือ กำเนิดสปีชีส์ ซึ่งได้อธิบายทฤษฎีวิวัฒนาการโดยกระบวนการคัดเลือกโดยธรรมชาติ[7] หลังการตีพิมพ์หนังสือไม่นาน ทฤษฎีของดาร์วินก็เป็นที่ยิมรับต่อสมาคมวิทยาศาสตร์ [8][9][10][11] ในคริสต์ทศวรรษที่ 1930 การคดเลือกโดยธรรมชาติของดาร์วินเริ่มมีความชัดเจนมากขึ้น หลังจากที่เกรเกอร์ เมนเดล ได้ค้นพบการถ่ายทอดลักษณะทางพันธุกรรม ก่อให้เกิดทฤษฎีวิวัฒนาการสมัยใหม่[12] โดยเมนเดลได้กล่าวถึงความสัมพันธ์ของ ยูนิต (ซึ่งภายหลังเรียกว่า ยีน) และ กระบวนการ ของการวิวัฒนาการ (การคัดเลือกโดยธรรมชาติ) การศึกษาของเมนเดลทำให้สามารถไขข้อข้องใจถึงวิธีการถ่ายทอดลักษณะทางพันธุกรรมจากกระบวนการคัดเลือกโดยธรรมชาติของดาร์วินได้อย่างดี และเป็นหลักการสำคัญของชีววิทยาสมัยใหม่ ซึ่งเป็นการอธิบายกระบวนการดังกล่าวร่วมกับความหลากหลายทางพันธุกรรมบนโลก[9][10][13]
การถ่ายทอดทางพันธุกรรม
[แก้]
วิวัฒนาการในสิ่งมีชีวิตเกิดขึ้นจากการแลกเปลี่ยนยีนระหว่างกระบวนการถ่ายทอดลักษณะทางพันธุกรรม ซึ่งปรากฏเป็นลักษณะเฉพาะของสิ่งมีชีวิต ในมนุษย์ ตัวอย่างเช่นสีของม่านตาเป็นหนึ่งในลักษณะของสิ่งมีชีวิตที่ถ่ายทอดได้ โดยแต่ละคนก็จะได้รับลักษณะดังกล่าวจากบิดามารดา[14] การถ่ายทอดลักษณะดังกล่าวควบคุมโดยยีน ยีนจะอยู่เป็นคู่บนโครโมโซมของสิ่งมีชีวิต และแสดงออกลักษณะทางพันธุกรรมเรียกว่า "จีโนไทป์" (genotype)[15]
ลักษณะของสิ่งมีชีวิตที่สร้างขึ้นอันประกอบด้วยลักษณะทางพันธุกรรม (จีโนไทป์) และพฤติกรรมอันเกิดจากการหล่อล้อมของสิ่งแวดล้อม รวมกันเรียกว่า "ฟีโนไทป์" (phenotype) ลักษณะที่สิ่งมีชีวิตแสดงออกก็จะการปฏิสัมพันธ์ร่วมกันระหว่างลักษณะทางพันธุกรรม (จีโนไทป์) และสิ่งแวดล้อม[16] ผลลัพธ์ก็คือ ไม่ใช่ทุกลักษณะของสิ่งมีชีวิต (ฟีโนไทป์) ที่จะสามารถถ่ายทอดลักษณะดังกล่าวสู่ลูกหลานได้ ตัวอย่างเช่น ลักษณะสีผิวของคนที่แดดส่องจนกลายเป็นสีแทน เป็นลักษณะที่เกิดร่วมกันระหว่างลักษณะพันธุกรรมแต่ละบุคคล (จีโนไทป์) ร่วมกับสิ่งแวดล้อม ดังนั้นลักษณะผิวสีแทนดังกล่าวจะไม่สามารถส่งผ่านไปยังรุ่นลูกได้ อย่างไรก็ตาม ผิวของคนทั่วไปก็มีปฏิกิริยาต่อแสงแดดแตกต่างกันไปขึ้นอยู่กับความแตกต่างของจีโนไทป์ อย่างไรก็ดีตัวอย่างดังกล่าวไม่มีผลต่อคนผิวเผือก เนื่องจากคนเหล่านี้ผิวหนังจะไม่มีปฏิกิริยากับแสงแดด[17]
ลักษณะการถ่ายทอดทางพันธุกรรมถ่ายทอดระหว่างดีเอ็นเอของแต่ละรุ่น อันเป็นโมเลกุลที่เก็บข้อมูลลักษณะ และรหัสพันธุกรรมของสิ่งมีชีวิต[15] ดีเอ็นเอเป็นสารพวกพอลิเมอร์ ประกอบด้วยเบส 4 ชนิด ลำดับเบสในดีเอ็นเอเรียงลำดับตามข้อมูลทางพันธุกรรม โดยใช้อักษรทางภาษาอังกฤษแทน อันได้แก่ A, T, C และ G ในการวิเคราะห์ข้อมูลทางคอมพิวเตอร์ ส่วนของโมเลกุลดีเอ็นเอที่ระบุหน้าที่ของยูนิตเรียกว่า "ยีน" แต่ละยีนก็จะมีลำดับเบสที่แตกต่างกันไป ในเซลล์ ประกอบไปด้วยดีเอ็นเอสายยาวรวมกันกับโปรตีนเป็นโครงสร้างรวมกันเรียกว่า "โครโมโซม" บริเวณจำเพาะที่อยู่ของโครโมโซมเรียกว่า "โลคัส" (locus) ลำดับของดีเอ็นเอ ณ ตำแหน่งโลคัสแตกต่างกันไปในแต่ละคน ทำให้เกิดรูปแบบที่แตกต่างกันในลำดับดังกล่าว เรียกว่า "อัลลีล" (allele) ลำดับดีเอ็นเอสามารถเปลี่ยนแปลงได้โดยผ่านการะบวนการกลายพันธุ์ ทำให้เกิดอัลลีลใหม่ ถ้ากระบวนการกลายพันธุ์เกิดขึ้นกับยีน อัลลีลใหม่จะส่งผลกระทบต่อลักษณะของสิ่งมีชีวิตอันเนื่องมาจากการควบคุมของยีน ทำให้เกิดการเปลี่ยนแปลงลักษณะฟีโนไทป์ของสิ่งมีชีวิต อย่างไรก็ตามความสอดคล้องระหว่างอัลลีล และลักษณะทางพันธุกรรมทำงานร่วมกันในบางกรณี แต่ลักษณะส่วนใหญ่จะซับซ้อน และเป็นลักษณะที่ควบคุมโดยยีนมากกว่า 1 ชนิด[18][19]
การแปรผัน
[แก้]ฟีโนไทป์ของสิ่งมีชีวิตแต่ละชนิดเป็นผลมาจากทั้งจีโนทไป์ และอิทธิพลจากสิ่งแวดล้อมที่สิ่งมีชีวิตนั้นอาศัยอยู่ ส่วนสำคัญของการแปรผันในฟีโนไทป์ในประชากรเกิดจากสามาเหตุที่แตกต่างกันระหว่างจีโนไทป์[19] ทฤษฎีวิวัฒนาการสมัยใหม่ให้คำจำกัดความถึงวิวัฒนาการในฐานะของการเปลี่ยนแปลงเป็นระยะเวลานานในความแปรผันทางพันธุกรรม ความถี่ของแต่ละแอลลีลจะผันแปร ความสัมพันธ์อาจแพร่หลายมากขึ้น หรือน้อยลง วิวัฒนาการเกิดขึ้นโดยการเปลี่ยนแปลงความถี่อัลลีลโดยวิธีใดวิธีหนึ่ง ความแปรผันจะหายไปเมื่ออัลลีลไปถึงจุดฟิกเซชัน (fixation) กล่าวคือเป็นลักษณะแปรผันดังกล่าวสูญหายไปจากประชากรหรือถูกแทนที่ด้วยลักษณะใหม่ที่ไม่เหมือนเช่นบรรพบุรุษ[20]
ความแปรผันเกิดขึ้นการกลายพันธุ์ในองค์ประกอบของยีน อาจเกิดจากการอพยพของประชากร (ยีนโฟลว์) หรือการจับคู่กันของยีนใหม่ๆในกระบวนการสืบพันธุ์ ความแปรผันยังอาจเกิดขึ้นจากการแลกเปลี่ยนยีนระหว่างสิ่งมีชีวิตต่างสปีชีส์ อาทิ การแลกเปลี่ยนยีนในแบคทีเรียและการไฮบริดในพืช[21] แม้ว่าจะเกิดการแลปเปลี่ยนยีนทำให้ความแปรผันเกิดความเปลี่ยนแปลงผ่านกระบวนการข้างต้น แต่จีโนมส่วนใหญ่ของสปีชีส์ก็ยังคงเอกลักษณ์จำเพาะแต่ละสปีชีส์ไว้[22] อย่างไรก็ดี แม้การเปลี่ยนแปลงเพียงเล็กน้อยในจีโนไทป์สามารถสร้างความเปลี่ยนแปลงอย่างมากต่อฟีโนไทป์ได้ อาทิ ชิมแปนซีและมนุษย์มีความแตกต่างของจีโฯมเพียง 5%[23]
การกลายพันธุ์
[แก้]
การแปรผันทางพันธุกรรมมีที่มาจากการกลายพันธุ์แบบสุ่ม โดยเกิดขึ้นในจีโนมของสิ่งมีชีวิต การกลายพันธุ์เป็นการเปลี่ยนลำดับดีเอ็นเอในจีโนมของเซลล์ มีหลากหลายสาเหตุ อาทิ การได้รับการฉายรังสี ไวรัส ทรานส์โพซัน และการได้รับสารเคมีที่มีผลต่อการเปลี่ยนแปลงทางพันธุกรรม นอกจากนี้อาจเกิดจากความผิดพลาดระหว่างกระบวนการแบ่งเซลล์แบบไมโอซิส หรือขั้นตอนการจำลองตัวของดีเอ็นเอ[24][25][26] These mutagens produce several different types of change in DNA sequences; these can either have no effect, alter the product of a gene, or prevent the gene from functioning. Studies in the fly Drosophila melanogaster suggest that if a mutation changes a protein produced by a gene, this will probably be harmful, with about 70 percent of these mutations having damaging effects, and the remainder being either neutral or weakly beneficial.[27] Due to the damaging effects that mutations can have on cells, organisms have evolved mechanisms such as DNA repair to remove mutations.[24] Therefore, the optimal mutation rate for a species is a trade-off between costs of a high mutation rate, such as deleterious mutations, and the metabolic costs of maintaining systems to reduce the mutation rate, such as DNA repair enzymes.[28] Some species such as retroviruses have such high mutation rates that most of their offspring will possess a mutated gene.[29] Such rapid mutation may have been selected so that these viruses can constantly and rapidly evolve, and thus evade the responses of the human immune system.[30]
Mutations can involve large sections of DNA becoming duplicated, which is a major source of raw material for evolving new genes, with tens to hundreds of genes duplicated in animal genomes every million years.[31] Most genes belong to larger families of genes of shared ancestry.[32] Novel genes are produced by several methods, commonly through the duplication and mutation of an ancestral gene, or by recombining parts of different genes to form new combinations with new functions.[33][34] Here, domains act as modules, each with a particular and independent function, that can be mixed together to produce genes encoding new proteins with novel properties.[35] For example, the human eye uses four genes to make structures that sense light: three for color vision and one for night vision; all four arose from a single ancestral gene.[36] An advantage of duplicating a gene (or even an entire genome) is that overlapping or redundant functions in multiple genes allows alleles to be retained that would otherwise be harmful, thus increasing genetic diversity.[37]
Changes in chromosome number may involve even larger mutations, where segments of the DNA within chromosomes break and then rearrange. For example, two chromosomes in the Homo genus fused to produce human chromosome 2; this fusion did not occur in the lineage of the other apes, and they retain these separate chromosomes.[38] In evolution, the most important role of such chromosomal rearrangements may be to accelerate the divergence of a population into new species by making populations less likely to interbreed, and thereby preserving genetic differences between these populations.[39]
Sequences of DNA that can move about the genome, such as transposons, make up a major fraction of the genetic material of plants and animals, and may have been important in the evolution of genomes.[40] For example, more than a million copies of the Alu sequence are present in the human genome, and these sequences have now been recruited to perform functions such as regulating gene expression.[41] Another effect of these mobile DNA sequences is that when they move within a genome, they can mutate or delete existing genes and thereby produce genetic diversity.[42]
Sex and recombination
[แก้]แม่แบบ:Details more In asexual organisms, genes are inherited together, or linked, as they cannot mix with genes in other organisms during reproduction. However, the offspring of sexual organisms contain random mixtures of their parents' chromosomes that are produced through independent assortment. In the related process of genetic recombination, sexual organisms can also exchange DNA between two matching chromosomes.[43] Recombination and reassortment do not alter allele frequencies, but instead change which alleles are associated with each other, producing offspring with new combinations of alleles.[44] While this process increases the variation in any individual's offspring, genetic mixing can be predicted to either have no effect, increase, or decrease the genetic variation in the population, depending on how the various alleles in the population are distributed. For example, if two alleles are randomly distributed in a population, then sex will have no effect on variation; however, if two alleles tend to be found as a pair, then genetic mixing will even out this non-random distribution and over time make the organisms in the population more similar to each other.[44] The overall effect of sex on natural variation remains unclear, but recent research suggests that sex usually increases genetic variation and may increase the rate of evolution.[45][46]
Recombination allows even alleles that are close together in a strand of DNA to be inherited independently. However, the rate of recombination is low, since in humans in a stretch of DNA one million base pairs long there is about a one in a hundred chance of a recombination event occurring per generation. As a result, genes close together on a chromosome may not always be shuffled away from each other, and genes that are close together tend to be inherited together.[47] This tendency is measured by finding how often two alleles of different genes occur together, which is called their linkage disequilibrium. A set of alleles that is usually inherited in a group is called a haplotype.
Sexual reproduction helps to remove harmful mutations and retain beneficial mutations.[48] Consequently, when alleles cannot be separated by recombination – such as in mammalian Y chromosomes, which pass intact from fathers to sons – harmful mutations accumulate.[49][50] In addition, recombination and reassortment can produce individuals with new and advantageous gene combinations. These positive effects are balanced by the fact that this process can cause mutations and separate beneficial combinations of genes.[48]
Population genetics
[แก้]From a genetic viewpoint, evolution is a generation-to-generation change in the frequencies of alleles within a population that shares a common gene pool.[51] A population is a localized group of individuals belonging to the same species. For example, all of the moths of the same species living in an isolated forest represent a population. A single gene in this population may have several alternate forms, which account for variations between the phenotypes of the organisms. An example might be a gene for coloration in moths that has two alleles: black and white. A gene pool is the complete set of alleles in a single population, so each allele occurs a certain number of times in a gene pool. The fraction of genes within the gene pool that are a particular allele is called the allele frequency. Evolution occurs when there are changes in the frequencies of alleles within a population of interbreeding organisms; for example the allele for black color in a population of moths becoming more common.
To understand the mechanisms that cause a population to evolve, it is useful to consider what conditions are required for a population not to evolve. The Hardy-Weinberg principle states that the frequencies of alleles (variations in a gene) in a sufficiently large population will remain constant if the only forces acting on that population are the random reshuffling of alleles during the formation of the sperm or egg, and the random combination of the alleles in these sex cells during fertilization.[52] Such a population is said to be in Hardy-Weinberg equilibrium - it is not evolving.[53]
กลไก
[แก้]กลไกหลักที่ก่อให้เกิดการวิวัฒนาการในรุ่นลูกหลาย ได้แก่ การคัดเลือกโดยธรรมชาติ, ความไม่แน่นอนทางพันธุกรรม (genetic drift) และ การไหลของยีน (gene flow) การคัดเลือกโดยธรรมชาติเป็นการพัฒนาความสามารถของสิ่งมีชีวิตเพื่อที่จะอยู่รอดและสืบพันธุ์ต่อไปได้ ส่วนความไม่แน่นอนทางพันธึกรรมคือการเปลี่ยนแปลงความถี่ของอัลลีล เนื่องมาจากการสุ่มตัวอย่างของยีนในช่วงของการสืบพันธุ์ และการไหลของยีนคือการส่งผ่านยีนภายในหรือระหว่างประชากร ความสัมพันธ์ที่สำคัฯขิงการคัดเลือกโดยธรรมชาติและความไม่แน่นอนทางพันธุกรรมในประชากรที่แตกต่างกันขึ้นอยู่กับความแข๋งแกร่งของการคัดสรรและผลกระทบจากขนาดของประชากร ซึ่งเป็นจำนวนของสิ่งมีชีวิตที่จะสามารถอยู่รอดได้[54] การคัดเลือกโดยธรรมชาติมักมีลักษณะที่เด่นกว่าในประชากรขนาดใหญ่ขณะที่ความไม่แน่นอนทางพันธุกรรมจะมีความโดดเด่นในประชากรขนาดเล็กซึ่งกระบวนการดังกล่าวช่วยซ่อมแซมการกลายพันธุ์ที่อันตราย[55] ผลลัพธ์คือการเปลี่ยนแปลงขนาดของกระชากรซึ่งมีผลกระทบอย่างมากต่อการวิวัฒนาการ ทำให้เกิดปรากฏการณ์คอขวดของประชากร[20] ปรากฏการณ์คอขวดอาจมีผลมาจากการเปลี่ยนแปลงการไหลของยีนเช่นการอพยพที่น้อยลง, การตั้งถิ่นฐานใหม่ของประชากรหรือประชากรส่วนย่อย[54]
การคัดเลือกโดยธรรมชาติ
[แก้]
การคัดเลือกโดยธรรมชาติคือกระบวนการผ่าเกล่าทางพันธุกรรมซึ่งเกิดขึ้นระหว่างการสืบพันธุ์จากรุ่นสู่รุ่น ซึ่งลักษณะผ่าเกล่าดังกล่าวจะแฝงและเปลี่ยนแปลงทีละเล็กละน้อย จึงไม่สามารถเห็นความแตกต่างในรุ่นใกล้เคียงกันของประชากร กระบวนการดังกล่าวเรียกอีกอย่างหนึ่งว่าเป็นกระบวนการที่มี "ความแจ้งชัดในตัว" (self-evident) ซึ่งดำรงภายใต้พื้นฐานความจริง 3 ประการ ได้แก่
- ความแปรผันทางพันธุกรรมจะเกิดขึ้นในประชาการของสิ่งมีชีวิต
- สิ่งมีชีวิตจะสืบพันธุ์ให้กำเนิดลูกหลานมากกว่าจำนวนที่สามารถอยู่รอดได้จริง
- ลูกหลานที่อยู่รอดจะมีความสามารถในการสืบพันธุ์
สภาวะดังกล่าทำให้เกิดการแข่งขันของสิ่งมีชีวิตเพื่อความอยู่รอดและสืบพันธุ์ ดังนั้นสิ่งมีชีวิตใดที่มีลักษณะที่เหมาะสมกับสภาพแวดล้อมนั้นๆ มากกว่า ก็จะสามารถต่อสู้และอยู่รอดในสภาวะแวดล้อมในขณะหนึ่งๆ และสืบพันธุ์เพื่อดำรงเผ่าพันธุ์ไว้ ลักษณะดังกล่าวเรียกได้ว่าได้รับการคัดเลือก ส่วนสิ่งมีชีวิตที่มีลักษณะไม่เหมาะสมกับสภาวะแวดล้อมในขณะหนึ่งๆ จะไม่สามารถอยู่รอดและสืบพันธุ์ต่อไปได้
แนวความคิดหลักของการคัดเลือกโดยธรรมชาติคือ "ความเหมาะสม" ทางวิวัฒนาการของสิ่งมีชีวิต ความเหมาะสมนี้จะเป็นสิ่งวัดว่าสิ่งมีชีวิตดังกล่าวจะสามารถดำรงอยู่เพื่อสืบพันธุ์สู่อีกรุ่นหนึ่งได้หรือไม่ อย่างไรก็ตามความเหมาะสมนี้ไม่ได้เกี่ยวข้องกับความสามารถในการสืบพันธุ์ แต่คือสัดส่วนของพันธุกรรมที่สืบทอดต่อในสิ่งมีชีวิตรุ่นต่อมา[56] นั่นคือ ถ้าอัลลีลใดเพิ่มขึ้นมากกว่าอัลลัลอื่นๆในยีน อัลลีลนั้นๆ จะกลายเป็นอัลลีลปกติของประชากรในรุ่นต่อๆมา คุณสมบัติดังกล่าวได้มีการนำมาพูดว่า "ถูกเลือก สำหรับ" อาทิ คุณสมบัติในการเพิ่มสมรรถภาพทางกายทำให้มีโอกาสอยู่รอดมากขึ้น และทำให้มีโอกาสเพิ่มจำนวนลูกหลานมากขึ้น ตรงข้ามกับคุณสมบัติที่หย่อนสมรรถภาพทางกายทำให้ไม่สามารถคงความได้เปรียบในระบบนิเวศได้และทำให้โอกาสสืบพันธุ์ให้ลูกหลานต่อไปต่ำลง ทำให้อัลลีลดังกล่าวมีลักษณะน้อยลง พวกนี้เรียกว่า "ถูกเลือกเพื่อ ต่อต้าน"[2] อย่างไรก็ดีลักษณะของความเหมาะสมของอัลลีลไม่ได้มีความคงตัว หากสิ่งแวดล้อมเปลี่ยนไป ลักษณะทางพันธุกรรมเดิมๆ อาจไม่สามารถคงความได้เปรียบในระบบนิเวศได้และลักษณะดังกล่าวอาจกลับทำให้เป็นอันตรายต่อสิ่งมีชีวิต[1].
การคัดเลือกโดยธรรมชาติในประชากรสำหรับลักษณะที่มีความแปรผันเชิงปริมาณ อาทิ ความสูง สามารถตัดประเภทใน 3 ประเภทที่แตกต่างกัน ประเภทแรกคือการคัดเลือกโดยตรง (directional selection) ซึ่งเป็นการเปลี่ยนแปลงโดยเฉลี่ยจากลักษณะดังกล่าวในหลายชั่วระยะเวลา อาทิ สิ่งมีชีวิตจะมีส่วนสูงเพิ่มขึ้นทีละน้อยๆ[57] ประเภทที่สองคือ การคัดเลือกความแตกต่าง สำหรับค่าความแตกต่างสองค่าที่ต่างกันมากและมักมีผลลัพธ์กลายเป็นค่าธรรมดาสองค่า โดยปฏิเสธค่าเฉลี่ย ลักษณะเช่นนี้อาจทำให้สิ่งมีชีวิตมีสองลักษณะคือเตี้ยและสูง แต่ไม่มีลักษณะที่พอดี ประเภทสุดท้ายคือการคัดเลือกความเสถียร (stabilizing selection) ซึ่งเป็นการปฏิเสธค่าสองค่าทีแตกต่างกันมาก ซึ่งทำให้สูญเสียลักษณะต่างๆ ระหว่างสองค่าที่แตกต่างกัน[58] อาทิ สิ่งมีชีวิตจะเพิ่มความสูงเป็นไปในลักษณะเดียวกันอย่างช้าๆ
กรณีพิเศษของกระบวนการคัดเลือกโดยธรรมชาติคือกระบวนการคัดเลือกโดยการสืบพันธุ์ (sexual selection) ซึ่งจะทำการคัดเลือกสิ่งมีชีวิตในเผ่าพันธุ์เดียวกันเพื่อจับคู่โดยอาศัยความดึงดูดจากสิ่งมีชีวิต[59] ลักษณะที่วิวัฒนาการผ่านกระบวนการคัดเลือกโดยสืบพันธุ์มีความโดดเด่นในเพศผู้สำหรับสิ่งมีชีวิตบางสายพันธุ์ แม้ว่าลักษณะบางอย่าง อาทิ ลักษณะของเขาสัตว์หรือการมีสีสันสดใสจะดึงดูดนักล่าและทำให้เพศผู้ที่รอดชีวิตมีจำนวนลดลง[60] ลักษณะที่เป็นข้อเสียเปรียบดังกล่าวมีการทำให้สมดุลด้วยความสำเร็จในการสืบพันธุ์ของเพศผู้ในอัตราที่สูงกว่าเพศเมีย[61]
โดยทั่วไปการคัดเลือกโดยธรรมชาติ Natural selection most generally makes nature the measure against which individuals, and individual traits, are more or less likely to survive. "Nature" in this sense refers to an ecosystem, that is, a system in which organisms interact with every other element, physical as well as biological, in their local environment. Eugene Odum, a founder of ecology, stated: "Any unit that includes all of the organisms (ie: the "community") in a given area interacting with the physical environment so that a flow of energy leads to clearly defined trophic structure, biotic diversity, and material cycles (ie: exchange of materials between living and nonliving parts) within the system is an ecosystem."[62] Each population within an ecosystem occupies a distinct niche, or position, with distinct relationships to other parts of the system. These relationships involve the life history of the organism, its position in the food chain, and its geographic range. This broad understanding of nature enables scientists to delineate specific forces which, together, comprise natural selection.
An active area of research is the unit of selection, with natural selection being proposed to work at the level of genes, cells, individual organisms, groups of organisms and even species.[63][64] None of these are mutually exclusive and selection may act on multiple levels simultaneously.[65] An example of selection occurring below the level of the individual organism are genes called transposons, which can replicate and spread throughout a genome.[66] Selection at a level above the individual, such as group selection, may allow the evolution of co-operation, as discussed below.[67]
Genetic drift
[แก้]
Genetic drift is the change in allele frequency from one generation to the next that occurs because alleles in offspring are a random sample of those in the parents, as well as from the role that chance plays in determining whether a given individual will survive and reproduce.[20] In mathematical terms, alleles are subject to sampling error. As a result, when selective forces are absent or relatively weak, allele frequencies tend to "drift" upward or downward randomly (in a random walk). This drift halts when an allele eventually becomes fixed, either by disappearing from the population, or replacing the other alleles entirely. Genetic drift may therefore eliminate some alleles from a population due to chance alone. Even in the absence of selective forces, genetic drift can cause two separate populations which began with the same genetic structure to drift apart into two divergent populations with different sets of alleles.[68]
The time for an allele to become fixed by genetic drift depends on population size, with fixation occurring more rapidly in smaller populations.[69] The precise measure of populations that is important here is called the effective population size, which was defined by Sewall Wright as a theoretical number representing the number of breeding individuals that would exhibit the same observed degree of inbreeding.
Although natural selection is responsible for adaptation, the relative importance of the two forces of natural selection and genetic drift in driving evolutionary change in general is an area of current research in evolutionary biology.[70] These investigations were prompted by the neutral theory of molecular evolution, which proposed that most evolutionary changes are the result of the fixation of neutral mutations that do not have any immediate effects on the fitness of an organism.[71] Hence, in this model, most genetic changes in a population are the result of constant mutation pressure and genetic drift.[72]
Gene flow
[แก้]
Gene flow is the exchange of genes between populations, which are usually of the same species.[73] Examples of gene flow within a species include the migration and then breeding of organisms, or the exchange of pollen. Gene transfer between species includes the formation of hybrid organisms and horizontal gene transfer.
Migration into or out of a population can change allele frequencies, as well as introducing genetic variation into a population. Immigration may add new genetic material to the established gene pool of a population. Conversely, emigration may remove genetic material. As barriers to reproduction between two diverging populations are required for the populations to become new species, gene flow may slow this process by spreading genetic differences between the populations. Gene flow is hindered by mountain ranges, oceans and deserts or even man-made structures such as the Great Wall of China, which has hindered the flow of plant genes.[74]
Depending on how far two species have diverged since their most recent common ancestor, it may still be possible for them to produce offspring, as with horses and donkeys mating to produce mules.[75] Such hybrids are generally infertile, due to the two different sets of chromosomes being unable to pair up during meiosis. In this case, closely related species may regularly interbreed, but hybrids will be selected against and the species will remain distinct. However, viable hybrids are occasionally formed and these new species can either have properties intermediate between their parent species, or possess a totally new phenotype.[76] The importance of hybridization in creating new species of animals is unclear, although cases have been seen in many types of animals,[77] with the gray tree frog being a particularly well-studied example.[78]
Hybridization is, however, an important means of speciation in plants, since polyploidy (having more than two copies of each chromosome) is tolerated in plants more readily than in animals.[79][80] Polyploidy is important in hybrids as it allows reproduction, with the two different sets of chromosomes each being able to pair with an identical partner during meiosis.[81] Polyploids also have more genetic diversity, which allows them to avoid inbreeding depression in small populations.[82]
Horizontal gene transfer is the transfer of genetic material from one organism to another organism that is not its offspring; this is most common among bacteria.[83] In medicine, this contributes to the spread of antibiotic resistance, as when one bacteria acquires resistance genes it can rapidly transfer them to other species.[84] Horizontal transfer of genes from bacteria to eukaryotes such as the yeast Saccharomyces cerevisiae and the adzuki bean beetle Callosobruchus chinensis may also have occurred.[85][86] An example of larger-scale transfers are the eukaryotic bdelloid rotifers, which appear to have received a range of genes from bacteria, fungi, and plants.[87] Viruses can also carry DNA between organisms, allowing transfer of genes even across biological domains.[88] Large-scale gene transfer has also occurred between the ancestors of eukaryotic cells and prokaryotes, during the acquisition of chloroplasts and mitochondrial.[89]
Outcomes
[แก้]Evolution influences every aspect of the form and behavior of organisms. Most prominent are the specific behavioral and physical adaptations that are the outcome of natural selection. These adaptations increase fitness by aiding activities such as finding food, avoiding predators or attracting mates. Organisms can also respond to selection by co-operating with each other, usually by aiding their relatives or engaging in mutually beneficial symbiosis. In the longer term, evolution produces new species through splitting ancestral populations of organisms into new groups that cannot or will not interbreed.
These outcomes of evolution are sometimes divided into macroevolution, which is evolution that occurs at or above the level of species, such as extinction and speciation, and microevolution, which is smaller evolutionary changes, such as adaptations, within a species or population. In general, macroevolution is regarded as the outcome of long periods of microevolution.[90] Thus, the distinction between micro- and macroevolution is not a fundamental one - the difference is simply the time involved.[91] However, in macroevolution, the traits of the entire species may be important. For instance, a large amount of variation among individuals allows a species to rapidly adapt to new habitats, lessening the chance of it going extinct, while a wide geographic range increases the chance of speciation, by making it more likely that part of the population will become isolated. In this sense, microevolution and macroevolution might involve selection at different levels - with microevolution acting on genes and organisms, versus macroevolutionary processes acting on entire species and affecting the rate of speciation and extinction.[92][93][94]
A common misconception is that evolution is "progressive," but natural selection has no long-term goal and does not necessarily produce greater complexity.[95][96] Although complex species have evolved, this occurs as a side effect of the overall number of organisms increasing, and simple forms of life remain more common.[97] For example, the overwhelming majority of species are microscopic prokaryotes, which form about half the world's biomass despite their small size,[98] and constitute the vast majority of Earth's biodiversity.[99] Simple organisms have therefore been the dominant form of life on Earth throughout its history and continue to be the main form of life up to the present day, with complex life only appearing more diverse because it is more noticeable.[100]
Adaptation
[แก้]Adaptations are structures or behaviors that enhance a specific function, causing organisms to become better at surviving and reproducing.[7] They are produced by a combination of the continuous production of small, random changes in traits, followed by natural selection of the variants best-suited for their environment.[101] This process can cause either the gain of a new feature, or the loss of an ancestral feature. An example that shows both types of change is bacterial adaptation to antibiotic selection, with genetic changes causing antibiotic resistance by both modifying the target of the drug, or increasing the activity of transporters that pump the drug out of the cell.[102] Other striking examples are the bacteria Escherichia coli evolving the ability to use citric acid as a nutrient in a long-term laboratory experiment,[103] Flavobacterium evolving a novel enzyme that allows these bacteria to grow on the by-products of nylon manufacturing,[104][105] and the soil bacterium Sphingobium evolving an entirely new metabolic pathway that degrades the synthetic pesticide pentachlorophenol.[106][107]
However, many traits that appear to be simple adaptations are in fact exaptations: structures originally adapted for one function, but which coincidentally became somewhat useful for some other function in the process.[108] One example is the African lizard Holaspis guentheri, which developed an extremely flat head for hiding in crevices, as can be seen by looking at its near relatives. However, in this species, the head has become so flattened that it assists in gliding from tree to tree—an exaptation.[108] Another is the recruitment of enzymes from glycolysis and xenobiotic metabolism to serve as structural proteins called crystallins within the lenses of organisms' eyes.[109][110]

As adaptation occurs through the gradual modification of existing structures, structures with similar internal organization may have very different functions in related organisms. This is the result of a single ancestral structure being adapted to function in different ways. The bones within bat wings, for example, are structurally similar to both human hands and seal flippers, due to the common descent of these structures from an ancestor that also had five digits at the end of each forelimb. Other idiosyncratic anatomical features, such as bones in the wrist of the panda being formed into a false "thumb," indicate that an organism's evolutionary lineage can limit what adaptations are possible.[112]
During adaptation, some structures may lose their original function and become vestigial structures.[113] Such structures may have little or no function in a current species, yet have a clear function in ancestral species, or other closely related species. Examples include pseudogenes,[114] the non-functional remains of eyes in blind cave-dwelling fish,[115] wings in flightless birds,[116] and the presence of hip bones in whales and snakes.[117] Examples of vestigial structures in humans include wisdom teeth,[118] the coccyx,[113] and the vermiform appendix.[113]
A critical principle of ecology is that of competitive exclusion: no two species can occupy the same niche in the same environment for a long time[119]. Consequently, natural selection will tend to force species to adapt to different ecological niches. This may mean that, for example, two species of cichlid fish adapt to live in different habitats, which will minimize the competition between them for food.[120]
An area of current investigation in evolutionary developmental biology is the developmental basis of adaptations and exaptations.[121] This research addresses the origin and evolution of embryonic development and how modifications of development and developmental processes produce novel features.[122] These studies have shown that evolution can alter development to create new structures, such as embryonic bone structures that develop into the jaw in other animals instead forming part of the middle ear in mammals.[123] It is also possible for structures that have been lost in evolution to reappear due to changes in developmental genes, such as a mutation in chickens causing embryos to grow teeth similar to those of crocodiles.[124] It is now becoming clear that most alterations in the form of organisms are due to changes in the level and timing of the expression of a small set of conserved genes.[125]
Co-evolution
[แก้]แม่แบบ:Details more Interactions between organisms can produce both conflict and co-operation. When the interaction is between pairs of species, such as a pathogen and a host, or a predator and its prey, these species can develop matched sets of adaptations. Here, the evolution of one species causes adaptations in a second species. These changes in the second species then, in turn, cause new adaptations in the first species. This cycle of selection and response is called co-evolution.[126] An example is the production of tetrodotoxin in the rough-skinned newt and the evolution of tetrodotoxin resistance in its predator, the common garter snake. In this predator-prey pair, an evolutionary arms race has produced high levels of toxin in the newt and correspondingly high levels of resistance in the snake.[127]
Co-operation
[แก้]แม่แบบ:Details more However, not all interactions between species involve conflict.[128] Many cases of mutually beneficial interactions have evolved. For instance, an extreme cooperation exists between plants and the mycorrhizal fungi that grow on their roots and aid the plant in absorbing nutrients from the soil.[129] This is a reciprocal relationship as the plants provide the fungi with sugars from photosynthesis. Here, the fungi actually grow inside plant cells, allowing them to exchange nutrients with their hosts, while sending signals that suppress the plant immune system.[130]
Coalitions between organisms of the same species have also evolved. An extreme case is the eusociality found in social insects, such as bees, termites and ants, where sterile insects feed and guard the small number of organisms in a colony that are able to reproduce. On an even smaller scale, the somatic cells that make up the body of an animal limit their reproduction so they can maintain a stable organism, which then supports a small number of the animal's germ cells to produce offspring. Here, somatic cells respond to specific signals that instruct them whether to grow, remain as they are, or die. If cells ignore these signals and multiply inappropriately, their uncontrolled growth causes cancer.[24]
These examples of cooperation within species are thought to have evolved through the process of kin selection, which is where one organism acts to help raise a relative's offspring.[131] This activity is selected for because if the helping individual contains alleles which promote the helping activity, it is likely that its kin will also contain these alleles and thus those alleles will be passed on.[132] Other processes that may promote cooperation include group selection, where cooperation provides benefits to a group of organisms.[133]
Speciation
[แก้]
Speciation is the process where a species diverges into two or more descendant species.[134] It has been observed multiple times under both controlled laboratory conditions and in nature.[135] In sexually reproducing organisms, speciation results from reproductive isolation followed by genealogical divergence. There are four mechanisms for speciation. The most common in animals is allopatric speciation, which occurs in populations initially isolated geographically, such as by habitat fragmentation or migration. Selection under these conditions can produce very rapid changes in the appearance and behaviour of organisms.[136][137] As selection and drift act independently on populations isolated from the rest of their species, separation may eventually produce organisms that cannot interbreed.[138]
The second mechanism of speciation is peripatric speciation, which occurs when small populations of organisms become isolated in a new environment. This differs from allopatric speciation in that the isolated populations are numerically much smaller than the parental population. Here, the founder effect causes rapid speciation through both rapid genetic drift and selection on a small gene pool.[139]
The third mechanism of speciation is parapatric speciation. This is similar to peripatric speciation in that a small population enters a new habitat, but differs in that there is no physical separation between these two populations. Instead, speciation results from the evolution of mechanisms that reduce gene flow between the two populations.[134] Generally this occurs when there has been a drastic change in the environment within the parental species' habitat. One example is the grass Anthoxanthum odoratum, which can undergo parapatric speciation in response to localized metal pollution from mines.[140] Here, plants evolve that have resistance to high levels of metals in the soil. Selection against interbreeding with the metal-sensitive parental population produces a change in flowering time of the metal-resistant plants, causing reproductive isolation. Selection against hybrids between the two populations may cause reinforcement, which is the evolution of traits that promote mating within a species, as well as character displacement, which is when two species become more distinct in appearance.[141]
Finally, in sympatric speciation species diverge without geographic isolation or changes in habitat. This form is rare since even a small amount of gene flow may remove genetic differences between parts of a population.[142] Generally, sympatric speciation in animals requires the evolution of both genetic differences and non-random mating, to allow reproductive isolation to evolve.[143]
One type of sympatric speciation involves cross-breeding of two related species to produce a new hybrid species. This is not common in animals as animal hybrids are usually sterile, because during meiosis the homologous chromosomes from each parent, being from different species cannot successfully pair. It is more common in plants, however because plants often double their number of chromosomes, to form polyploids. This allows the chromosomes from each parental species to form a matching pair during meiosis, as each parent's chromosomes is represented by a pair already.[144] An example of such a speciation event is when the plant species Arabidopsis thaliana and Arabidopsis arenosa cross-bred to give the new species Arabidopsis suecica.[145] This happened about 20,000 years ago,[146] and the speciation process has been repeated in the laboratory, which allows the study of the genetic mechanisms involved in this process.[147] Indeed, chromosome doubling within a species may be a common cause of reproductive isolation, as half the doubled chromosomes will be unmatched when breeding with undoubled organisms.[80]
Speciation events are important in the theory of punctuated equilibrium, which accounts for the pattern in the fossil record of short "bursts" of evolution interspersed with relatively long periods of stasis, where species remain relatively unchanged.[148] In this theory, speciation and rapid evolution are linked, with natural selection and genetic drift acting most strongly on organisms undergoing speciation in novel habitats or small populations. As a result, the periods of stasis in the fossil record correspond to the parental population, and the organisms undergoing speciation and rapid evolution are found in small populations or geographically restricted habitats, and therefore rarely being preserved as fossils.[149]
Extinction
[แก้]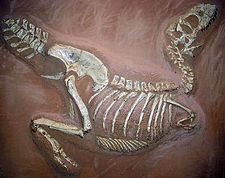
Extinction is the disappearance of an entire species. Extinction is not an unusual event, as species regularly appear through speciation, and disappear through extinction.[150] Indeed, virtually all animal and plant species that have lived on earth are now extinct,[151] and extinction appears to be the ultimate fate of all species.[152] These extinctions have happened continuously throughout the history of life, although the rate of extinction spikes in occasional mass extinction events.[153] The Cretaceous–Tertiary extinction event, during which the dinosaurs went extinct, is the most well-known, but the earlier Permian–Triassic extinction event was even more severe, with approximately 96 percent of species driven to extinction.[153] The Holocene extinction event is an ongoing mass extinction associated with humanity's expansion across the globe over the past few thousand years. Present-day extinction rates are 100-1000 times greater than the background rate, and up to 30 percent of species may be extinct by the mid 21st century.[154] Human activities are now the primary cause of the ongoing extinction event;[155] global warming may further accelerate it in the future.[156]
The role of extinction in evolution depends on which type is considered. The causes of the continuous "low-level" extinction events, which form the majority of extinctions, are not well understood and may be the result of competition between species for limited resources (competitive exclusion).[12] If competition from other species does alter the probability that a species will become extinct, this could produce species selection as a level of natural selection.[63] The intermittent mass extinctions are also important, but instead of acting as a selective force, they drastically reduce diversity in a nonspecific manner and promote bursts of rapid evolution and speciation in survivors.[153]
Evolutionary history of life
[แก้]Origin of life
[แก้]แม่แบบ:Details more The origin of life is a necessary precursor for biological evolution, but understanding that evolution occurred once organisms appeared and investigating how this happens does not depend on understanding exactly how life began.[157] The current scientific consensus is that the complex biochemistry that makes up life came from simpler chemical reactions, but it is unclear how this occurred.[158] Not much is certain about the earliest developments in life, the structure of the first living things, or the identity and nature of any last universal common ancestor or ancestral gene pool.[159][160] Consequently, there is no scientific consensus on how life began, but proposals include self-replicating molecules such as RNA,[161] and the assembly of simple cells.[162]
Common descent
[แก้]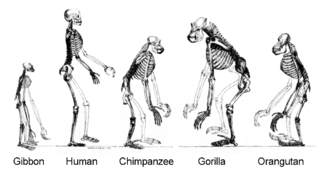
All organisms on Earth are descended from a common ancestor or ancestral gene pool.[163] Current species are a stage in the process of evolution, with their diversity the product of a long series of speciation and extinction events.[164] The common descent of organisms was first deduced from four simple facts about organisms: First, they have geographic distributions that cannot be explained by local adaptation. Second, the diversity of life is not a set of completely unique organisms, but organisms that share morphological similarities. Third, vestigial traits with no clear purpose resemble functional ancestral traits, and finally, that organisms can be classified using these similarities into a hierarchy of nested groups.[7]
Past species have also left records of their evolutionary history. Fossils, along with the comparative anatomy of present-day organisms, constitute the morphological, or anatomical, record.[165] By comparing the anatomies of both modern and extinct species, paleontologists can infer the lineages of those species. However, this approach is most successful for organisms that had hard body parts, such as shells, bones or teeth. Further, as prokaryotes such as bacteria and archaea share a limited set of common morphologies, their fossils do not provide information on their ancestry.
More recently, evidence for common descent has come from the study of biochemical similarities between organisms. For example, all living cells use the same basic set of nucleotides and amino acids.[166] The development of molecular genetics has revealed the record of evolution left in organisms' genomes: dating when species diverged through the molecular clock produced by mutations.[167] For example, these DNA sequence comparisons have revealed the close genetic similarity between humans and chimpanzees and shed light on when the common ancestor of these species existed.[168]
Evolution of life
[แก้]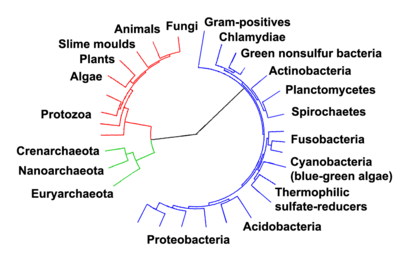
Despite the uncertainty on how life began, it is generally accepted that prokaryotes inhabited the Earth from approximately 3–4 billion years ago.[170][171] No obvious changes in morphology or cellular organization occurred in these organisms over the next few billion years.[172]
The eukaryotes were the next major development in cell evolution. These came from ancient bacteria being engulfed by the ancestors of eukaryotic cells, in a cooperative association called endosymbiosis.[89][173] The engulfed bacteria and the host cell then underwent co-evolution, with the bacteria evolving into either mitochondria or hydrogenosomes.[174] An independent second engulfment of cyanobacterial-like organisms led to the formation of chloroplasts in algae and plants.[175] It is unknown when the first eukaryotic cells appeared though they first emerged between 1.6 - 2.7 billion years ago.
The history of life was that of the unicellular eukaryotes, prokaryotes, and archaea until about 610 million years ago when multicellular organisms began to appear in the oceans in the Ediacaran period.[170][176] The evolution of multicellularity occurred in multiple independent events, in organisms as diverse as sponges, brown algae, cyanobacteria, slime moulds and myxobacteria.[177]
Soon after the emergence of these first multicellular organisms, a remarkable amount of biological diversity appeared over approximately 10 million years, in an event called the Cambrian explosion. Here, the majority of types of modern animals appeared in the fossil record, as well as unique lineages that subsequently became extinct.[178] Various triggers for the Cambrian explosion have been proposed, including the accumulation of oxygen in the atmosphere from photosynthesis.[179] About 500 million years ago, plants and fungi colonized the land, and were soon followed by arthropods and other animals.[180] Amphibians first appeared around 300 million years ago, followed by early amniotes, then mammals around 200 million years ago and birds around 100 million years ago (both from "reptile"-like lineages). However, despite the evolution of these large animals, smaller organisms similar to the types that evolved early in this process continue to be highly successful and dominate the Earth, with the majority of both biomass and species being prokaryotes.[99]
History of evolutionary thought
[แก้]
Evolutionary ideas such as common descent and the transmutation of species have existed since at least the 6th century BC, when they were expounded by the Greek philosopher Anaximander.[181] Others who considered such ideas included the Greek philosopher Empedocles, the Roman philosopher-poet Lucretius, the Arab biologist Al-Jahiz,[182] the Persian philosopher Ibn Miskawayh, the Brethren of Purity,[183] and the Eastern philosopher Zhuangzi.[184] As biological knowledge grew in the 18th century, evolutionary ideas were set out by a few natural philosophers including Pierre Maupertuis in 1745 and Erasmus Darwin in 1796.[185] The ideas of the biologist Jean-Baptiste Lamarck about transmutation of species had wide influence. Charles Darwin formulated his idea of natural selection in 1838 and was still developing his theory in 1858 when Alfred Russel Wallace sent him a similar theory, and both were presented to the Linnean Society of London in separate papers.[186] At the end of 1859 Darwin's publication of On the Origin of Species explained natural selection in detail and presented evidence leading to increasingly wide acceptance of the occurrence of evolution.
Debate about the mechanisms of evolution continued, and Darwin could not explain the source of the heritable variations which would be acted on by natural selection. Like Lamarck, he thought that parents passed on adaptations acquired during their lifetimes,[187] a theory which was subsequently dubbed Lamarckism.[188] In the 1880s August Weismann's experiments indicated that changes from use and disuse were not heritable, and Lamarckism gradually fell from favour.[189][190] More significantly, Darwin could not account for how traits were passed down from generation to generation. In 1865 Gregor Mendel found that traits were inherited in a predictable manner.[191] When Mendel's work was rediscovered in 1900s, disagreements over the rate of evolution predicted by early geneticists and biometricians led to a rift between the Mendelian and Darwinian models of evolution.
Yet it was the rediscovery of Gregor Mendel’s pioneering work on the fundamentals of genetics (of which Darwin and Wallace were unaware) by Hugo de Vries and others in the early 1900s that provided the impetus for a better understanding of how variation occurs in plant and animal traits. That variation is the main fuel used by natural selection to shape the wide variety of adaptive traits observed in organic life. Even though Hugo de Vries and other early geneticists were very critical of the theory of evolution, their rediscovery of and subsequent work on genetics eventually provided a solid basis on which the theory of evolution stood even more convincingly than when it was originally proposed.[192]
The apparent contradiction between Darwin’s theory of evolution by natural selection and Mendel’s work was reconciled in the 1920s and 1930s by evolutionary biologists such as J.B.S. Haldane, Sewall Wright, and particularly Ronald Fisher, who set the foundations for the establishment of the field of population genetics. The end result was a combination of evolution by natural selection and Mendelian inheritance, the modern evolutionary synthesis.[193] In the 1940s, the identification of DNA as the genetic material by Oswald Avery and colleagues and the subsequent publication of the structure of DNA by James Watson and Francis Crick in 1953, demonstrated the physical basis for inheritance. Since then, genetics and molecular biology have become core parts of evolutionary biology and have revolutionized the field of phylogenetics.[12]
In its early history, evolutionary biology primarily drew in scientists from traditional taxonomically oriented disciplines, whose specialist training in particular organisms addressed general questions in evolution. As evolutionary biology expanded as an academic discipline, particularly after the development of the modern evolutionary synthesis, it began to draw more widely from the biological sciences.[12] Currently the study of evolutionary biology involves scientists from fields as diverse as biochemistry, ecology, genetics and physiology, and evolutionary concepts are used in even more distant disciplines such as psychology, medicine, philosophy and computer science.
Social and cultural responses
[แก้]
In the 19th century, particularly after the publication of On the Origin of Species, the idea that life had evolved was an active source of academic debate centered on the philosophical, social and religious implications of evolution. Nowadays, the fact that organisms evolve is uncontested in the scientific literature and the modern evolutionary synthesis is widely accepted by scientists. However, evolution remains a contentious concept for some religious groups.[195]
While many religions and denominations have reconciled their beliefs with evolution through various concepts of theistic evolution, there are many creationists who believe that evolution is contradicted by the creation myths found in their respective religions.[196] As Darwin recognized early on, the most controversial aspect of evolutionary biology is its implications for human origins. In some countries—notably the United States—these tensions between science and religion have fueled the ongoing creation–evolution controversy, a religious conflict focusing on politics and public education.[197] While other scientific fields such as cosmology[198] and earth science[199] also conflict with literal interpretations of many religious texts, evolutionary biology experiences significantly more opposition from religious literalists.
Another example associated with evolutionary theory that is now widely regarded as unwarranted is misnamed "Social Darwinism," a term given to the 19th century Whig Malthusian theory developed by Herbert Spencer into ideas about "survival of the fittest" in commerce and human societies as a whole, and by others into claims that social inequality, racism, and imperialism were justified.[200] However, these ideas contradict Darwin's own views, and contemporary scientists and philosophers consider these ideas to be neither mandated by evolutionary theory nor supported by data.[201][202]
Applications
[แก้]A major technological application of evolution is artificial selection, which is the intentional selection of certain traits in a population of organisms. Humans have used artificial selection for thousands of years in the domestication of plants and animals.[203] More recently, such selection has become a vital part of genetic engineering, with selectable markers such as antibiotic resistance genes being used to manipulate DNA in molecular biology.
As evolution can produce highly optimized processes and networks, it has many applications in computer science. Here, simulations of evolution using evolutionary algorithms and artificial life started with the work of Nils Aall Barricelli in the 1960s, and was extended by Alex Fraser, who published a series of papers on simulation of artificial selection.[204] Artificial evolution became a widely recognized optimization method as a result of the work of Ingo Rechenberg in the 1960s and early 1970s, who used evolution strategies to solve complex engineering problems.<ref>{{cite book |last=Rechenberg |first=Ingo |year=19
อ้างอิง
[แก้]- ↑ 1.0 1.1 1.2 Futuyma, Douglas J. (2005). Evolution. Sunderland, Massachusetts: Sinauer Associates, Inc. ISBN 0-87893-187-2.
- ↑ 2.0 2.1 Lande R, Arnold SJ (1983). "The measurement of selection on correlated characters". Evolution. 37: 1210–26}. doi:10.2307/2408842.
- ↑ Ayala FJ (2007). "Darwin's greatest discovery: design without designer". Proc. Natl. Acad. Sci. U.S.A. 104 Suppl 1: 8567–73. doi:10.1073/pnas.0701072104. PMID 17494753.
- ↑ แม่แบบ:Wikiref
- ↑ Ian C. Johnston (1999). "History of Science: Early Modern Geology". Malaspina University-College. สืบค้นเมื่อ 2008-01-15.
- ↑ Bowler, Peter J. (2003). Evolution:The History of an Idea. University of California Press. ISBN 0-52023693-9.
- ↑ 7.0 7.1 7.2 Darwin, Charles (1859). On the Origin of Species (1st ed.). London: John Murray. p. 1.. Related earlier ideas were acknowledged in Darwin, Charles (1861). On the Origin of Species (3rd ed.). London: John Murray. xiii.
- ↑ AAAS Council (December 26, 1922). "AAAS Resolution: Present Scientific Status of the Theory of Evolution". American Association for the Advancement of Science.
- ↑ 9.0 9.1 "IAP Statement on the Teaching of Evolution" (PDF). The Interacademy Panel on International Issues. 2006. สืบค้นเมื่อ 2007-04-25. Joint statement issued by the national science academies of 67 countries, including the United Kingdom's Royal Society
- ↑ 10.0 10.1 Board of Directors, American Association for the Advancement of Science (2006-02-16). "Statement on the Teaching of Evolution" (PDF). American Association for the Advancement of Science. from the world's largest general scientific society
- ↑ "Statements from Scientific and Scholarly Organizations". National Center for Science Education.
- ↑ 12.0 12.1 12.2 12.3 Kutschera U, Niklas K (2004). "The modern theory of biological evolution: an expanded synthesis". Naturwissenschaften. 91 (6): 255–76. doi:10.1007/s00114-004-0515-y. PMID 15241603.
- ↑ "Special report on evolution". New Scientist. 2008-01-19.
- ↑ Sturm RA, Frudakis TN (2004). "Eye colour: portals into pigmentation genes and ancestry". Trends Genet. 20 (8): 327–32. doi:10.1016/j.tig.2004.06.010. PMID 15262401.
- ↑ 15.0 15.1 Pearson H (2006). "Genetics: what is a gene?". Nature. 441 (7092): 398–401. doi:10.1038/441398a. PMID 16724031.
- ↑ Peaston AE, Whitelaw E (2006). "Epigenetics and phenotypic variation in mammals". Mamm. Genome. 17 (5): 365–74. doi:10.1007/s00335-005-0180-2. PMID 16688527.
- ↑ Oetting WS, Brilliant MH, King RA (1996). "The clinical spectrum of albinism in humans". Molecular medicine today. 2 (8): 330–35. doi:10.1016/1357-4310(96)81798-9. PMID 8796918.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Mayeux R (2005). "Mapping the new frontier: complex genetic disorders". J. Clin. Invest. 115 (6): 1404–07. doi:10.1172/JCI25421. PMID 15931374.
- ↑ 19.0 19.1 Wu R, Lin M (2006). "Functional mapping - how to map and study the genetic architecture of dynamic complex traits". Nat. Rev. Genet. 7 (3): 229–37. doi:10.1038/nrg1804. PMID 16485021.
- ↑ 20.0 20.1 20.2 Harwood AJ (1998). "Factors affecting levels of genetic diversity in natural populations". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 177–86. doi:10.1098/rstb.1998.0200. PMID 9533122.
- ↑ Draghi J, Turner P (2006). "DNA secretion and gene-level selection in bacteria". Microbiology (Reading, Engl.). 152 (Pt 9): 2683–8. PMID 16946263.
*Mallet J (2007). "Hybrid speciation". Nature. 446 (7133): 279–83. doi:10.1038/nature05706. PMID 17361174. - ↑ Butlin RK, Tregenza T (1998). "Levels of genetic polymorphism: marker loci versus quantitative traits". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 187–98. doi:10.1098/rstb.1998.0201. PMID 9533123.
- ↑ Wetterbom A, Sevov M, Cavelier L, Bergström TF (2006). "Comparative genomic analysis of human and chimpanzee indicates a key role for indels in primate evolution". J. Mol. Evol. 63 (5): 682–90. doi:10.1007/s00239-006-0045-7. PMID 17075697.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 24.0 24.1 24.2 Bertram J (2000). "The molecular biology of cancer". Mol. Aspects Med. 21 (6): 167–223. doi:10.1016/S0098-2997(00)00007-8. PMID 11173079.
- ↑ Aminetzach YT, Macpherson JM, Petrov DA (2005). "Pesticide resistance via transposition-mediated adaptive gene truncation in Drosophila". Science. 309 (5735): 764–67. doi:10.1126/science.1112699. PMID 16051794.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Burrus V, Waldor M (2004). "Shaping bacterial genomes with integrative and conjugative elements". Res. Microbiol. 155 (5): 376–86. doi:10.1016/j.resmic.2004.01.012. PMID 15207870.
- ↑ Sawyer SA, Parsch J, Zhang Z, Hartl DL (2007). "Prevalence of positive selection among nearly neutral amino acid replacements in Drosophila". Proc. Natl. Acad. Sci. U.S.A. 104 (16): 6504–10. doi:10.1073/pnas.0701572104. PMID 17409186.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Sniegowski P, Gerrish P, Johnson T, Shaver A (2000). "The evolution of mutation rates: separating causes from consequences". Bioessays. 22 (12): 1057–66. doi:10.1002/1521-1878(200012)22:12<1057::AID-BIES3>3.0.CO;2-W. PMID 11084621.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Drake JW, Charlesworth B, Charlesworth D, Crow JF (1998). "Rates of spontaneous mutation". Genetics. 148 (4): 1667–86. PMID 9560386.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Holland J, Spindler K, Horodyski F, Grabau E, Nichol S, VandePol S (1982). "Rapid evolution of RNA genomes". Science. 215 (4540): 1577–85. doi:10.1126/science.7041255. PMID 7041255.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Carroll SB, Grenier J, Weatherbee SD (2005). From DNA to Diversity: Molecular Genetics and the Evolution of Animal Design. Second Edition. Oxford: Blackwell Publishing. ISBN 1-4051-1950-0.
{{cite book}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Harrison P, Gerstein M (2002). "Studying genomes through the aeons: protein families, pseudogenes and proteome evolution". J Mol Biol. 318 (5): 1155–74. doi:10.1016/S0022-2836(02)00109-2. PMID 12083509.
- ↑ Orengo CA, Thornton JM (2005). "Protein families and their evolution-a structural perspective". Annu. Rev. Biochem. 74: 867–900. doi:10.1146/annurev.biochem.74.082803.133029. PMID 15954844.
- ↑ Long M, Betrán E, Thornton K, Wang W (November 2003). "The origin of new genes: glimpses from the young and old". Nat. Rev. Genet. 4 (11): 865–75. doi:10.1038/nrg1204. PMID 14634634.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Wang M, Caetano-Anollés G (2009). "The evolutionary mechanics of domain organization in proteomes and the rise of modularity in the protein world". Structure. 17 (1): 66–78. doi:doi:10.1016/j.str.2008.11.008.
{{cite journal}}: ตรวจสอบค่า|doi=(help) - ↑ Bowmaker JK (1998). "Evolution of colour vision in vertebrates". Eye (London, England). 12 (Pt 3b): 541–47. PMID 9775215.
- ↑ Gregory TR, Hebert PD (1999). "The modulation of DNA content: proximate causes and ultimate consequences". Genome Res. 9 (4): 317–24. PMID 10207154.
- ↑ Zhang J, Wang X, Podlaha O (2004). "Testing the chromosomal speciation hypothesis for humans and chimpanzees". Genome Res. 14 (5): 845–51. doi:10.1101/gr.1891104. PMID 15123584.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Ayala FJ, Coluzzi M (2005). "Chromosome speciation: humans, Drosophila, and mosquitoes". Proc. Natl. Acad. Sci. U.S.A. 102 Supplement 1: 6535–42. doi:10.1073/pnas.0501847102. PMID 15851677.
- ↑ Hurst GD, Werren JH (2001). "The role of selfish genetic elements in eukaryotic evolution". Nat. Rev. Genet. 2 (8): 597–606. doi:10.1038/35084545. PMID 11483984.
- ↑ Häsler J, Strub K (2006). "Alu elements as regulators of gene expression". Nucleic Acids Res. 34 (19): 5491–97. doi:10.1093/nar/gkl706. PMID 17020921.
- ↑ Aminetzach YT, Macpherson JM, Petrov DA (2005). "Pesticide resistance via transposition-mediated adaptive gene truncation in Drosophila". Science. 309 (5735): 764–67. doi:10.1126/science.1112699. PMID 16051794.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Radding C (1982). "Homologous pairing and strand exchange in genetic recombination". Annu. Rev. Genet. 16: 405–37. doi:10.1146/annurev.ge.16.120182.002201. PMID 6297377.
- ↑ 44.0 44.1 Agrawal AF (2006). "Evolution of sex: why do organisms shuffle their genotypes?". Curr. Biol. 16 (17): R696. doi:10.1016/j.cub.2006.07.063. PMID 16950096.
- ↑ Peters AD, Otto SP (2003). "Liberating genetic variance through sex". Bioessays. 25 (6): 533–7. doi:10.1002/bies.10291. PMID 12766942.
- ↑ Goddard MR, Godfray HC, Burt A (2005). "Sex increases the efficacy of natural selection in experimental yeast populations". Nature. 434 (7033): 636–40. doi:10.1038/nature03405. PMID 15800622.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Lien S, Szyda J, Schechinger B, Rappold G, Arnheim N (2000). "Evidence for heterogeneity in recombination in the human pseudoautosomal region: high resolution analysis by sperm typing and radiation-hybrid mapping". Am. J. Hum. Genet. 66 (2): 557–66. doi:10.1086/302754. PMID 10677316.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 48.0 48.1 Otto S (2003). "The advantages of segregation and the evolution of sex". Genetics. 164 (3): 1099–118. PMID 12871918.
- ↑ Muller H (1964). "The relation of recombination to mutational advance". Mutat. Res. 106: 2–9. PMID 14195748.
- ↑ Charlesworth B, Charlesworth D (2000). "The degeneration of Y chromosomes". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 355 (1403): 1563–72. doi:10.1098/rstb.2000.0717. PMID 11127901.
- ↑ Stoltzfus A (2006). "Mutationism and the dual causation of evolutionary change". Evol. Dev. 8 (3): 304–17. doi:10.1111/j.1525-142X.2006.00101.x. PMID 16686641.
- ↑ O'Neil, Dennis (2008). "Hardy-Weinberg Equilibrium Model". The synthetic theory of evolution: An introduction to modern evolutionary concepts and theories. Behavioral Sciences Department, Palomar College. สืบค้นเมื่อ 2008-01-06.
- ↑ Bright, Kerry (2006). "Causes of evolution". Teach Evolution and Make It Relevant. National Science Foundation. สืบค้นเมื่อ 2007-12-30.
- ↑ 54.0 54.1 Whitlock M (2003). "Fixation probability and time in subdivided populations". Genetics. 164 (2): 767–79. PMID 12807795.
- ↑ Ohta T (2002). "Near-neutrality in evolution of genes and gene regulation". PNAS. 99 (25): 16134–37. doi:10.1073/pnas.252626899. PMID 12461171.
- ↑ Haldane J (1959). "The theory of natural selection today". Nature. 183 (4663): 710–13. doi:10.1038/183710a0. PMID 13644170.
- ↑ Hoekstra H, Hoekstra J, Berrigan D, Vignieri S, Hoang A, Hill C, Beerli P, Kingsolver J (2001). "Strength and tempo of directional selection in the wild". Proc. Natl. Acad. Sci. U.S.A. 98 (16): 9157–60. doi:10.1073/pnas.161281098. PMID 11470913.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Felsenstein (1979). "Excursions along the Interface between Disruptive and Stabilizing Selection". Genetics. 93 (3): 773–95. PMID 17248980.
- ↑ Andersson M, Simmons L (2006). "Sexual selection and mate choice". Trends Ecol. Evol. (Amst.). 21 (6): 296–302. doi:10.1016/j.tree.2006.03.015. PMID 16769428.
- ↑ Kokko H, Brooks R, McNamara J, Houston A (2002). "The sexual selection continuum". Proc. Biol. Sci. 269 (1498): 1331–40. doi:10.1098/rspb.2002.2020. PMID 12079655.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Hunt J, Brooks R, Jennions M, Smith M, Bentsen C, Bussière L (2004). "High-quality male field crickets invest heavily in sexual display but die young". Nature. 432 (7020): 1024–27. doi:10.1038/nature03084. PMID 15616562.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Odum, EP (1971) Fundamentals of ecology, third edition, Saunders New York
- ↑ 63.0 63.1 Gould SJ (1998). "Gulliver's further travels: the necessity and difficulty of a hierarchical theory of selection". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 307–14. doi:10.1098/rstb.1998.0211. PMID 9533127.
- ↑ Mayr E (1997). "The objects of selection". Proc. Natl. Acad. Sci. U.S.A. 94 (6): 2091–94. doi:10.1073/pnas.94.6.2091. PMID 9122151.
- ↑ Maynard Smith J (1998). "The units of selection". Novartis Found. Symp. 213: 203–11, discussion 211–17. PMID 9653725.
- ↑ Hickey DA (1992). "Evolutionary dynamics of transposable elements in prokaryotes and eukaryotes". Genetica. 86 (1–3): 269–74. doi:10.1007/BF00133725. PMID 1334911.
- ↑ Gould SJ, Lloyd EA (1999). "Individuality and adaptation across levels of selection: how shall we name and generalize the unit of Darwinism?". Proc. Natl. Acad. Sci. U.S.A. 96 (21): 11904–09. doi:10.1073/pnas.96.21.11904. PMID 10518549.
- ↑ Lande R (1989). "Fisherian and Wrightian theories of speciation". Genome. 31 (1): 221–27. PMID 2687093.
- ↑ Otto S, Whitlock M (1997). "The probability of fixation in populations of changing size". Genetics. 146 (2): 723–33. PMID 9178020.
- ↑ Nei M (2005). "Selectionism and neutralism in molecular evolution". Mol. Biol. Evol. 22 (12): 2318–42. doi:10.1093/molbev/msi242. PMID 16120807.
- ↑ Kimura M (1991). "The neutral theory of molecular evolution: a review of recent evidence". Jpn. J. Genet. 66 (4): 367–86. doi:10.1266/jjg.66.367. PMID 1954033.
- ↑ Kimura M (1989). "The neutral theory of molecular evolution and the world view of the neutralists". Genome. 31 (1): 24–31. PMID 2687096.
- ↑ Morjan C, Rieseberg L (2004). "How species evolve collectively: implications of gene flow and selection for the spread of advantageous alleles". Mol. Ecol. 13 (6): 1341–56. doi:10.1111/j.1365-294X.2004.02164.x. PMID 15140081.
- ↑ Su H, Qu L, He K, Zhang Z, Wang J, Chen Z, Gu H (2003). "The Great Wall of China: a physical barrier to gene flow?". Heredity. 90 (3): 212–19. doi:10.1038/sj.hdy.6800237. PMID 12634804.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Short RV (1975). "The contribution of the mule to scientific thought". J. Reprod. Fertil. Suppl. (23): 359–64. PMID 1107543.
- ↑ Gross B, Rieseberg L (2005). "The ecological genetics of homoploid hybrid speciation". J. Hered. 96 (3): 241–52. doi:10.1093/jhered/esi026. PMID 15618301.
- ↑ Burke JM, Arnold ML (2001). "Genetics and the fitness of hybrids". Annu. Rev. Genet. 35: 31–52. doi:10.1146/annurev.genet.35.102401.085719. PMID 11700276.
- ↑ Vrijenhoek RC (2006). "Polyploid hybrids: multiple origins of a treefrog species". Curr. Biol. 16 (7): R245. doi:10.1016/j.cub.2006.03.005. PMID 16581499.
- ↑ Wendel J (2000). "Genome evolution in polyploids". Plant Mol. Biol. 42 (1): 225–49. doi:10.1023/A:1006392424384. PMID 10688139.
- ↑ 80.0 80.1 Sémon M, Wolfe KH (2007). "Consequences of genome duplication". Curr Opin Genet Dev. 17 (6): 505–12. doi:10.1016/j.gde.2007.09.007. PMID 18006297.
- ↑ Comai L (2005). "The advantages and disadvantages of being polyploid". Nat. Rev. Genet. 6 (11): 836–46. doi:10.1038/nrg1711. PMID 16304599.
- ↑ Soltis P, Soltis D (2000). "The role of genetic and genomic attributes in the success of polyploids". Proc. Natl. Acad. Sci. U.S.A. 97 (13): 7051–57. doi:10.1073/pnas.97.13.7051. PMID 10860970.
- ↑ Boucher Y, Douady CJ, Papke RT, Walsh DA, Boudreau ME, Nesbo CL, Case RJ, Doolittle WF (2003). "Lateral gene transfer and the origins of prokaryotic groups". Annu Rev Genet. 37: 283–328. doi:10.1146/annurev.genet.37.050503.084247. PMID 14616063.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Walsh T (2006). "Combinatorial genetic evolution of multiresistance". Curr. Opin. Microbiol. 9 (5): 476–82. doi:10.1016/j.mib.2006.08.009. PMID 16942901.
- ↑ Kondo N, Nikoh N, Ijichi N, Shimada M, Fukatsu T (2002). "Genome fragment of Wolbachia endosymbiont transferred to X chromosome of host insect". Proc. Natl. Acad. Sci. U.S.A. 99 (22): 14280–85. doi:10.1073/pnas.222228199. PMID 12386340.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Sprague G (1991). "Genetic exchange between kingdoms". Curr. Opin. Genet. Dev. 1 (4): 530–33. doi:10.1016/S0959-437X(05)80203-5. PMID 1822285.
- ↑ Gladyshev EA, Meselson M, Arkhipova IR (May 2008). "Massive horizontal gene transfer in bdelloid rotifers". Science (journal). 320 (5880): 1210–3. doi:10.1126/science.1156407. PMID 18511688.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Baldo A, McClure M (1999). "Evolution and horizontal transfer of dUTPase-encoding genes in viruses and their hosts". J. Virol. 73 (9): 7710–21. PMID 10438861.
- ↑ 89.0 89.1 Poole A, Penny D (2007). "Evaluating hypotheses for the origin of eukaryotes". Bioessays. 29 (1): 74–84. doi:10.1002/bies.20516. PMID 17187354.
- ↑ Hendry AP, Kinnison MT (2001). "An introduction to microevolution: rate, pattern, process". Genetica. 112–113: 1–8. doi:10.1023/A:1013368628607. PMID 11838760.
- ↑ Leroi AM (2000). "The scale independence of evolution". Evol. Dev. 2 (2): 67–77. doi:10.1046/j.1525-142x.2000.00044.x. PMID 11258392.
- ↑ แม่แบบ:Wikiref
- ↑ Gould SJ (July 1994). "Tempo and mode in the macroevolutionary reconstruction of Darwinism". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6764–71. PMC 44281. PMID 8041695.
- ↑ Jablonski, D. (2000). "Micro- and macroevolution: scale and hierarchy in evolutionary biology and paleobiology". Paleobiology. 26 (sp4): 15–52. doi:10.1666/0094-8373(2000)26[15:MAMSAH]2.0.CO;2.
- ↑ Michael J. Dougherty. Is the human race evolving or devolving? Scientific American July 20, 1998.
- ↑ TalkOrigins Archive response to Creationist claims - Claim CB932: Evolution of degenerate forms
- ↑ Carroll SB (2001). "Chance and necessity: the evolution of morphological complexity and diversity". Nature. 409 (6823): 1102–09. doi:10.1038/35059227. PMID 11234024.
- ↑ Whitman W, Coleman D, Wiebe W (1998). "Prokaryotes: the unseen majority". Proc Natl Acad Sci U S a. 95 (12): 6578–83. doi:10.1073/pnas.95.12.6578. PMID 9618454.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 99.0 99.1 Schloss P, Handelsman J (2004). "Status of the microbial census". Microbiol Mol Biol Rev. 68 (4): 686–91. doi:10.1128/MMBR.68.4.686-691.2004. PMID 15590780.
- ↑ Nealson K (1999). "Post-Viking microbiology: new approaches, new data, new insights". Orig Life Evol Biosph. 29 (1): 73–93. doi:10.1023/A:1006515817767. PMID 11536899.
- ↑ Orr H (2005). "The genetic theory of adaptation: a brief history". Nat. Rev. Genet. 6 (2): 119–27. doi:10.1038/nrg1523. PMID 15716908.
- ↑ Nakajima A, Sugimoto Y, Yoneyama H, Nakae T (2002). "High-level fluoroquinolone resistance in Pseudomonas aeruginosa due to interplay of the MexAB-OprM efflux pump and the DNA gyrase mutation". Microbiol. Immunol. 46 (6): 391–95. PMID 12153116.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Blount ZD, Borland CZ, Lenski RE (June 2008). "Inaugural Article: Historical contingency and the evolution of a key innovation in an experimental population of Escherichia coli". Proc. Natl. Acad. Sci. U.S.A. 105 (23): 7899–7906. doi:10.1073/pnas.0803151105. PMID 18524956.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Okada H, Negoro S, Kimura H, Nakamura S (1983). "Evolutionary adaptation of plasmid-encoded enzymes for degrading nylon oligomers". Nature. 306 (5939): 203–6. doi:10.1038/306203a0. PMID 6646204.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Ohno S (April 1984). "Birth of a unique enzyme from an alternative reading frame of the preexisted, internally repetitious coding sequence". Proc. Natl. Acad. Sci. U.S.A. 81 (8): 2421–5. doi:10.1073/pnas.81.8.2421. PMC 345072. PMID 6585807.
- ↑ Copley SD (June 2000). "Evolution of a metabolic pathway for degradation of a toxic xenobiotic: the patchwork approach". Trends Biochem. Sci. 25 (6): 261–5. PMID 10838562.
- ↑ Crawford RL, Jung CM, Strap JL (October 2007). "The recent evolution of pentachlorophenol (PCP)-4-monooxygenase (PcpB) and associated pathways for bacterial degradation of PCP". Biodegradation. 18 (5): 525–39. doi:10.1007/s10532-006-9090-6. PMID 17123025.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 108.0 108.1 แม่แบบ:Wikiref
- ↑ Piatigorsky J, Kantorow M, Gopal-Srivastava R, Tomarev SI (1994). "Recruitment of enzymes and stress proteins as lens crystallins". EXS. 71: 241–50. PMID 8032155.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Wistow G (August 1993). "Lens crystallins: gene recruitment and evolutionary dynamism". Trends Biochem. Sci. 18 (8): 301–6. doi:10.1016/0968-0004(93)90041-K. PMID 8236445.
- ↑ Bejder L, Hall BK (2002). "Limbs in whales and limblessness in other vertebrates: mechanisms of evolutionary and developmental transformation and loss". Evol. Dev. 4 (6): 445–58. doi:10.1046/j.1525-142X.2002.02033.x. PMID 12492145.
- ↑ Salesa MJ, Antón M, Peigné S, Morales J (2006). "Evidence of a false thumb in a fossil carnivore clarifies the evolution of pandas". Proc. Natl. Acad. Sci. U.S.A. 103 (2): 379–82. doi:10.1073/pnas.0504899102. PMID 16387860.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 113.0 113.1 113.2 Fong D, Kane T, Culver D (1995). "Vestigialization and Loss of Nonfunctional Characters". Ann. Rev. Ecol. Syst. 26: 249–68. doi:10.1146/annurev.es.26.110195.001341.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Zhang Z, Gerstein M (August 2004). "Large-scale analysis of pseudogenes in the human genome". Curr. Opin. Genet. Dev. 14 (4): 328–35. doi:10.1016/j.gde.2004.06.003. PMID 15261647.
- ↑ Jeffery WR (2005). "Adaptive evolution of eye degeneration in the Mexican blind cavefish". J. Hered. 96 (3): 185–96. doi:10.1093/jhered/esi028. PMID 15653557.
- ↑ Maxwell EE, Larsson HC (2007). "Osteology and myology of the wing of the Emu (Dromaius novaehollandiae), and its bearing on the evolution of vestigial structures". J. Morphol. 268 (5): 423–41. doi:10.1002/jmor.10527. PMID 17390336.
- ↑ Bejder L, Hall BK (2002). "Limbs in whales and limblessness in other vertebrates: mechanisms of evolutionary and developmental transformation and loss". Evol. Dev. 4 (6): 445–58. doi:10.1046/j.1525-142X.2002.02033.x. PMID 12492145.
- ↑ Silvestri AR, Singh I (2003). "The unresolved problem of the third molar: would people be better off without it?". Journal of the American Dental Association (1939). 134 (4): 450–55. doi:10.1146/annurev.es.26.110195.001341. PMID 12733778.
- ↑ Hardin, G. (1960). The Competitive Exclusion Principle. Science 131, 1292-1297.
- ↑ Kocher TD (April 2004). "Adaptive evolution and explosive speciation: the cichlid fish model" (PDF). Nat. Rev. Genet. 5 (4): 288–98. doi:10.1038/nrg1316. PMID 15131652.
- ↑ Johnson NA, Porter AH (2001). "Toward a new synthesis: population genetics and evolutionary developmental biology". Genetica. 112–113: 45–58. doi:10.1023/A:1013371201773. PMID 11838782.
- ↑ Baguñà J, Garcia-Fernàndez J (2003). "Evo-Devo: the long and winding road". Int. J. Dev. Biol. 47 (7–8): 705–13. PMID 14756346.
*Gilbert SF (2003). "The morphogenesis of evolutionary developmental biology". Int. J. Dev. Biol. 47 (7–8): 467–77. PMID 14756322. - ↑ Allin EF (1975). "Evolution of the mammalian middle ear". J. Morphol. 147 (4): 403–37. doi:10.1002/jmor.1051470404. PMID 1202224.
- ↑ Harris MP, Hasso SM, Ferguson MW, Fallon JF (2006). "The development of archosaurian first-generation teeth in a chicken mutant". Curr. Biol. 16 (4): 371–77. doi:10.1016/j.cub.2005.12.047. PMID 16488870.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Carroll SB (July 2008). "Evo-devo and an expanding evolutionary synthesis: a genetic theory of morphological evolution". Cell. 134 (1): 25–36. doi:10.1016/j.cell.2008.06.030. PMID 18614008.
- ↑ Wade MJ (2007). "The co-evolutionary genetics of ecological communities". Nat. Rev. Genet. 8 (3): 185–95. doi:10.1038/nrg2031. PMID 17279094.
- ↑ Geffeney S, Brodie ED, Ruben PC, Brodie ED (2002). "Mechanisms of adaptation in a predator-prey arms race: TTX-resistant sodium channels". Science. 297 (5585): 1336–9. doi:10.1126/science.1074310. PMID 12193784.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์)
*Brodie ED, Ridenhour BJ, Brodie ED (2002). "The evolutionary response of predators to dangerous prey: hotspots and coldspots in the geographic mosaic of coevolution between garter snakes and newts". Evolution. 56 (10): 2067–82. PMID 12449493.{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Sachs J (2006). "Cooperation within and among species". J. Evol. Biol. 19 (5): 1415–8, discussion 1426–36. doi:10.1111/j.1420-9101.2006.01152.x. PMID 16910971.
*Nowak M (2006). "Five rules for the evolution of cooperation". Science. 314 (5805): 1560–63. doi:10.1126/science.1133755. PMID 17158317. - ↑ Paszkowski U (2006). "Mutualism and parasitism: the yin and yang of plant symbioses". Curr. Opin. Plant Biol. 9 (4): 364–70. doi:10.1016/j.pbi.2006.05.008. PMID 16713732.
- ↑ Hause B, Fester T (2005). "Molecular and cell biology of arbuscular mycorrhizal symbiosis". Planta. 221 (2): 184–96. doi:10.1007/s00425-004-1436-x. PMID 15871030.
- ↑ Reeve HK, Hölldobler B (2007). "The emergence of a superorganism through intergroup competition". Proc Natl Acad Sci U S A. 104 (23): 9736–40. doi:10.1073/pnas.0703466104. PMID 17517608.
- ↑ Axelrod R, Hamilton W (2005). "The evolution of cooperation". Science. 211 (4489): 1390–96. doi:10.1126/science.7466396. PMID 7466396.
- ↑ Wilson EO, Hölldobler B (2005). "Eusociality: origin and consequences". Proc. Natl. Acad. Sci. U.S.A. 102 (38): 13367–71. doi:10.1073/pnas.0505858102. PMID 16157878.
- ↑ 134.0 134.1 Gavrilets S (2003). "Perspective: models of speciation: what have we learned in 40 years?". Evolution. 57 (10): 2197–215. doi:10.1554/02-727. PMID 14628909.
- ↑ Rice, W.R. (1993). "Laboratory experiments on speciation: what have we learned in 40 years". Evolution. 47 (6): 1637–1653. doi:10.2307/2410209. สืบค้นเมื่อ 2008-05-19.
{{cite journal}}: ไม่รู้จักพารามิเตอร์|coauthors=ถูกละเว้น แนะนำ (|author=) (help)
*Jiggins CD, Bridle JR (2004). "Speciation in the apple maggot fly: a blend of vintages?". Trends Ecol. Evol. (Amst.). 19 (3): 111–4. doi:10.1016/j.tree.2003.12.008. PMID 16701238.
*Boxhorn, J (1995). "Observed Instances of Speciation". TalkOrigins Archive. สืบค้นเมื่อ 2008-12-26.
*Weinberg JR, Starczak VR, Jorg, D (1992). "Evidence for Rapid Speciation Following a Founder Event in the Laboratory". Evolution. 46 (4): 1214–20. doi:10.2307/2409766.{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Herrel, A.; Huyghe, K.; Vanhooydonck, B.; Backeljau, T.; Breugelmans, K.; Grbac, I.; Van Damme, R.; Irschick, D.J. (2008). "Rapid large-scale evolutionary divergence in morphology and performance associated with exploitation of a different dietary resource". Proceedings of the National Academy of Sciences. 105 (12): 4792–5. doi:10.1073/pnas.0711998105. PMID 18344323.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Losos, J.B. Warhelt, K.I. Schoener, T.W. (1997). "Adaptive differentiation following experimental island colonization in Anolis lizards". Nature. 387 (6628): 70–73. doi:10.1038/387070a0.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Hoskin CJ, Higgle M, McDonald KR, Moritz C (2005). "Reinforcement drives rapid allopatric speciation". Nature. 437: 1353–356. doi:10.1038/nature04004.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Templeton AR (1980). "The theory of speciation via the founder principle". Genetics. 94 (4): 1011–38. PMID 6777243.
- ↑ Antonovics J (2006). "Evolution in closely adjacent plant populations X: long-term persistence of prereproductive isolation at a mine boundary". Heredity. 97 (1): 33–37. doi:10.1038/sj.hdy.6800835. PMID 16639420.
- ↑ Nosil P, Crespi B, Gries R, Gries G (2007). "Natural selection and divergence in mate preference during speciation". Genetica. 129 (3): 309–27. doi:10.1007/s10709-006-0013-6. PMID 16900317.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Savolainen V, Anstett M-C, Lexer C, Hutton I, Clarkson JJ, Norup MV, Powell MP, Springate D, Salamin N, Baker WJr (2006). "Sympatric speciation in palms on an oceanic island". Nature. 441: 210–13. doi:10.1038/nature04566. PMID 16467788.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์)
*Barluenga M, Stölting KN, Salzburger W, Muschick M, Meyer A (2006). "Sympatric speciation in Nicaraguan crater lake cichlid fish". Nature. 439: 719–723. doi:10.1038/nature04325. PMID 16467837.{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Gavrilets S (2006). "The Maynard Smith model of sympatric speciation". J. Theor. Biol. 239 (2): 172–82. doi:10.1016/j.jtbi.2005.08.041. PMID 16242727.
- ↑ Hegarty Mf, Hiscock SJ (2008). "Genomic clues to the evolutionary success of polyploid plants". Current Biology. 18 (10): 435–44. doi:10.1016/j.cub.2008.03.043.
- ↑ Jakobsson M, Hagenblad J, Tavaré S; และคณะ (2006). "A unique recent origin of the allotetraploid species Arabidopsis suecica: Evidence from nuclear DNA markers". Mol. Biol. Evol. 23 (6): 1217–31. doi:10.1093/molbev/msk006. PMID 16549398.
{{cite journal}}: ใช้ et al. อย่างชัดเจน ใน|author=(help)CS1 maint: multiple names: authors list (ลิงก์) - ↑ Säll T, Jakobsson M, Lind-Halldén C, Halldén C (2003). "Chloroplast DNA indicates a single origin of the allotetraploid Arabidopsis suecica". J. Evol. Biol. 16 (5): 1019–29. doi:10.1046/j.1420-9101.2003.00554.x. PMID 14635917.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Bomblies K, Weigel D (2007). "Arabidopsis-a model genus for speciation". Curr Opin Genet Dev. 17 (6): 500–504. doi:10.1016/j.gde.2007.09.006. PMID 18006296.
- ↑ Niles Eldredge and Stephen Jay Gould, 1972. "Punctuated equilibria: an alternative to phyletic gradualism" In T.J.M. Schopf, ed., Models in Paleobiology. San Francisco: Freeman Cooper. pp. 82-115. Reprinted in N. Eldredge Time frames. Princeton: Princeton Univ. Press. 1985
- ↑ Gould SJ (1994). "Tempo and mode in the macroevolutionary reconstruction of Darwinism". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6764–71. doi:10.1073/pnas.91.15.6764. PMID 8041695.
- ↑ Benton MJ (1995). "Diversification and extinction in the history of life". Science. 268 (5207): 52–58. doi:10.1126/science.7701342. PMID 7701342.
- ↑ Raup DM (1986). "Biological extinction in earth history". Science. 231: 1528–33. doi:10.1126/science.11542058. PMID 11542058.
- ↑ Avise JC, Hubbell SP, Ayala FJ. (2008). "In the light of evolution II: Biodiversity and extinction". Proc. Natl. Acad. Sci. U.S.A. 105 (S1): 11453–11457. doi:10.1073/pnas.0802504105. PMID 18695213.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 153.0 153.1 153.2 Raup DM (1994). "The role of extinction in evolution" (PDF). Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6758–63. doi:10.1073/pnas.91.15.6758. PMID 8041694.
- ↑ Novacek MJ, Cleland EE (2001). "The current biodiversity extinction event: scenarios for mitigation and recovery". Proc. Natl. Acad. Sci. U.S.A. 98 (10): 5466–70. doi:10.1073/pnas.091093698. PMID 11344295.
- ↑ Pimm S, Raven P, Peterson A, Sekercioglu CH, Ehrlich PR (2006). "Human impacts on the rates of recent, present, and future bird extinctions". Proc. Natl. Acad. Sci. U.S.A. 103 (29): 10941–6. doi:10.1073/pnas.0604181103. PMID 16829570.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์)
*Barnosky AD, Koch PL, Feranec RS, Wing SL, Shabel AB (2004). "Assessing the causes of late Pleistocene extinctions on the continents". Science. 306 (5693): 70–05. doi:10.1126/science.1101476. PMID 15459379.{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Lewis OT (2006). "Climate change, species-area curves and the extinction crisis" (PDF). Philos. Trans. R. Soc. Lond., B, Biol. Sci. 361 (1465): 163–71. doi:10.1098/rstb.2005.1712. PMID 16553315.
- ↑ Isaak, Mark (2005). "Claim CB090: Evolution without abiogenesis". TalkOrigins Archive. สืบค้นเมื่อ 2008-12-26.
- ↑ Peretó J (2005). "Controversies on the origin of life" (PDF). Int. Microbiol. 8 (1): 23–31. PMID 15906258.
- ↑ Luisi PL, Ferri F, Stano P (2006). "Approaches to semi-synthetic minimal cells: a review". Naturwissenschaften. 93 (1): 1–13. doi:10.1007/s00114-005-0056-z. PMID 16292523.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Trevors JT, Abel DL (2004). "Chance and necessity do not explain the origin of life". Cell Biol. Int. 28 (11): 729–39. doi:10.1016/j.cellbi.2004.06.006. PMID 15563395.Forterre P, Benachenhou-Lahfa N, Confalonieri F, Duguet M, Elie C, Labedan B (1992). "The nature of the last universal ancestor and the root of the tree of life, still open questions". BioSystems. 28 (1–3): 15–32. doi:10.1016/0303-2647(92)90004-I. PMID 1337989.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Joyce GF (2002). "The antiquity of RNA-based evolution". Nature. 418 (6894): 214–21. doi:10.1038/418214a. PMID 12110897.
- ↑ Trevors JT, Psenner R (2001). "From self-assembly of life to present-day bacteria: a possible role for nanocells". FEMS Microbiol. Rev. 25 (5): 573–82. doi:10.1111/j.1574-6976.2001.tb00592.x. PMID 11742692.
- ↑ Penny D, Poole A (1999). "The nature of the last universal common ancestor". Curr. Opin. Genet. Dev. 9 (6): 672–77. doi:10.1016/S0959-437X(99)00020-9. PMID 10607605.
- ↑ Bapteste E, Walsh DA (2005). "Does the 'Ring of Life' ring true?". Trends Microbiol. 13 (6): 256–61. doi:10.1016/j.tim.2005.03.012. PMID 15936656.
- ↑ Jablonski D (1999). "The future of the fossil record". Science. 284 (5423): 2114–16. doi:10.1126/science.284.5423.2114. PMID 10381868.
- ↑ Mason SF (1984). "Origins of biomolecular handedness". Nature. 311 (5981): 19–23. doi:10.1038/311019a0. PMID 6472461.
- ↑ Wolf YI, Rogozin IB, Grishin NV, Koonin EV (2002). "Genome trees and the tree of life". Trends Genet. 18 (9): 472–79. doi:10.1016/S0168-9525(02)02744-0. PMID 12175808.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Varki A, Altheide TK (2005). "Comparing the human and chimpanzee genomes: searching for needles in a haystack". Genome Res. 15 (12): 1746–58. doi:10.1101/gr.3737405. PMID 16339373.
- ↑ Ciccarelli FD, Doerks T, von Mering C, Creevey CJ, Snel B, Bork P (2006). "Toward automatic reconstruction of a highly resolved tree of life". Science. 311 (5765): 1283–87. doi:10.1126/science.1123061. PMID 16513982.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ 170.0 170.1 Cavalier-Smith T (2006). "Cell evolution and Earth history: stasis and revolution" (PDF). Philos Trans R Soc Lond B Biol Sci. 361 (1470): 969–1006. doi:10.1098/rstb.2006.1842. PMID 16754610.
- ↑ Schopf J (2006). "Fossil evidence of Archaean life". Philos Trans R Soc Lond B Biol Sci. 361 (1470): 869–85. doi:10.1098/rstb.2006.1834. PMID 16754604.
*Altermann W, Kazmierczak J (2003). "Archean microfossils: a reappraisal of early life on Earth". Res Microbiol. 154 (9): 611–17. doi:10.1016/j.resmic.2003.08.006. PMID 14596897. - ↑ Schopf J (1994). "Disparate rates, differing fates: tempo and mode of evolution changed from the Precambrian to the Phanerozoic". Proc Natl Acad Sci U S a. 91 (15): 6735–42. doi:10.1073/pnas.91.15.6735. PMID 8041691.
- ↑ Dyall S, Brown M, Johnson P (2004). "Ancient invasions: from endosymbionts to organelles". Science. 304 (5668): 253–57. doi:10.1126/science.1094884. PMID 15073369.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Martin W (2005). "The missing link between hydrogenosomes and mitochondria". Trends Microbiol. 13 (10): 457–59. doi:10.1016/j.tim.2005.08.005. PMID 16109488.
- ↑ Lang B, Gray M, Burger G (1999). "Mitochondrial genome evolution and the origin of eukaryotes". Annu Rev Genet. 33: 351–97. doi:10.1146/annurev.genet.33.1.351. PMID 10690412.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์)
*McFadden G (1999). "Endosymbiosis and evolution of the plant cell". Curr Opin Plant Biol. 2 (6): 513–19. doi:10.1016/S1369-5266(99)00025-4. PMID 10607659. - ↑ DeLong E, Pace N (2001). "Environmental diversity of bacteria and archaea". Syst Biol. 50 (4): 470–8. doi:10.1080/106351501750435040. PMID 12116647.
- ↑ Kaiser D (2001). "Building a multicellular organism". Annu. Rev. Genet. 35: 103–23. doi:10.1146/annurev.genet.35.102401.090145. PMID 11700279.
- ↑ Valentine JW, Jablonski D, Erwin DH (1999). "Fossils, molecules and embryos: new perspectives on the Cambrian explosion". Development. 126 (5): 851–9. PMID 9927587.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Ohno S (1997). "The reason for as well as the consequence of the Cambrian explosion in animal evolution". J. Mol. Evol. 44 Suppl 1: S23–7. doi:10.1007/PL00000055. PMID 9071008.
*Valentine J, Jablonski D (2003). "Morphological and developmental macroevolution: a paleontological perspective". Int. J. Dev. Biol. 47 (7–8): 517–22. PMID 14756327. - ↑ Waters ER (2003). "Molecular adaptation and the origin of land plants". Mol. Phylogenet. Evol. 29 (3): 456–63. doi:10.1016/j.ympev.2003.07.018. PMID 14615186.
- ↑ Wright, S (1984). Evolution and the Genetics of Populations, Volume 1: Genetic and Biometric Foundations. The University of Chicago Press. ISBN 0-226-91038-5.
- ↑ Zirkle C (1941). "Natural Selection before the "Origin of Species"". Proceedings of the American Philosophical Society. 84 (1): 71–123.
- ↑ Muhammad Hamidullah and Afzal Iqbal (1993), The Emergence of Islam: Lectures on the Development of Islamic World-view, Intellectual Tradition and Polity, p. 143-144. Islamic Research Institute, Islamabad.
- ↑ "A Source Book In Chinese Philosophy", Chan, Wing-Tsit, p. 204, 1962.
- ↑ Terrall, M (2002). The Man Who Flattened the Earth: Maupertuis and the Sciences in the Enlightenment. The University of Chicago Press. ISBN 978-0226793610.
- ↑ Wallace, A (1858). "On the Tendency of Species to form Varieties, and on the Perpetuation of Varieties and Species by Natural Means of Selection". Journal of the Proceedings of the Linnean Society of London. Zoology. 3: 53–62. doi:10.1098/rsnr.2006.0171. สืบค้นเมื่อ 2007-05-13.
{{cite journal}}: ไม่รู้จักพารามิเตอร์|coauthors=ถูกละเว้น แนะนำ (|author=) (help) - ↑ Darwin, Charles (1872). "Effects of the increased Use and Disuse of Parts, as controlled by Natural Selection". The Origin of Species. 6th edition, p. 108. John Murray. สืบค้นเมื่อ 2007-12-28.
- ↑ Leakey, Richard E.; Darwin, Charles (1979). The illustrated origin of species. London: Faber. ISBN 0-571-14586-8.
{{cite book}}: CS1 maint: multiple names: authors list (ลิงก์) p. 17-18 - ↑ Ghiselin, Michael T. (September/October 1994), "Nonsense in schoolbooks: 'The Imaginary Lamarck'", The Textbook Letter, The Textbook League, สืบค้นเมื่อ 2008-01-23
{{citation}}: ตรวจสอบค่าวันที่ใน:|publication-date=(help) - ↑ Magner, LN (2002). A History of the Life Sciences, Third Edition, Revised and Expanded. CRC. ISBN 978-0824708245.
- ↑ Weiling F (1991). "Historical study: Johann Gregor Mendel 1822–1884". Am. J. Med. Genet. 40 (1): 1–25, discussion 26. doi:10.1002/ajmg.1320400103. PMID 1887835.
- ↑ Quammen, D. (2006). The reluctant Mr. Darwin: An intimate portrait of Charles Darwin and the making of his theory of evolution. New York, NY: W.W. Norton & Company.
- ↑ Bowler, Peter J. (1989). The Mendelian Revolution: The Emergence of Hereditarian Concepts in Modern Science and Society. Baltimore: Johns Hopkins University Press. ISBN 978-0801838880.
- ↑ Browne, Janet (2003). Charles Darwin: The Power of Place. London: Pimlico. pp. 376–379. ISBN 0-7126-6837-3.
- ↑ For an overview of the philosophical, religious, and cosmological controversies, see: Dennett, D (1995). Darwin's Dangerous Idea: Evolution and the Meanings of Life. Simon & Schuster. ISBN 978-0684824710.
*For the scientific and social reception of evolution in the 19th and early 20th centuries, see: Johnston, Ian C. "History of Science: Origins of Evolutionary Theory". And Still We Evolve. Liberal Studies Department, Malaspina University College. สืบค้นเมื่อ 2007-05-24.
*Bowler, PJ (2003). Evolution: The History of an Idea, Third Edition, Completely Revised and Expanded. University of California Press. ISBN 978-0520236936.
*Zuckerkandl E (2006). "Intelligent design and biological complexity". Gene. 385: 2–18. doi:10.1016/j.gene.2006.03.025. PMID 17011142. - ↑ Ross, M.R. (2005). "Who Believes What? Clearing up Confusion over Intelligent Design and Young-Earth Creationism" (PDF). Journal of Geoscience Education. 53 (3): 319. สืบค้นเมื่อ 2008-04-28.
- ↑ Spergel D. N. (2006). "Science communication. Public acceptance of evolution". Science. 313 (5788): 765–66. doi:10.1126/science.1126746. PMID 16902112.
- ↑ Spergel, D. N. (2003). "First-Year Wilkinson Microwave Anisotropy Probe (WMAP) Observations: Determination of Cosmological Parameters". The Astrophysical Journal Supplement Series. 148: 175–94. doi:10.1086/377226.
{{cite journal}}: ไม่รู้จักพารามิเตอร์|coauthors=ถูกละเว้น แนะนำ (|author=) (help) - ↑ Wilde SA, Valley JW, Peck WH, Graham CM (2001). "Evidence from detrital zircons for the existence of continental crust and oceans on the Earth 4.4 Gyr ago". Nature. 409 (6817): 175–78. doi:10.1038/35051550. PMID 11196637.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ On the history of eugenics and evolution, see Kevles, D (1998). In the Name of Eugenics: Genetics and the Uses of Human Heredity. Harvard University Press. ISBN 978-0674445574.
- ↑ Darwin strongly disagreed with attempts by Herbert Spencer and others to extrapolate evolutionary ideas to all possible subjects; see Midgley, M (2004). The Myths we Live By. Routledge. p. 62. ISBN 978-0415340779.
- ↑ Allhoff F (2003). "Evolutionary ethics from Darwin to Moore". History and philosophy of the life sciences. 25 (1): 51–79. doi:10.1080/03919710312331272945. PMID 15293515.
- ↑ Doebley JF, Gaut BS, Smith BD (2006). "The molecular genetics of crop domestication". Cell. 127 (7): 1309–21. doi:10.1016/j.cell.2006.12.006. PMID 17190597.
{{cite journal}}: CS1 maint: multiple names: authors list (ลิงก์) - ↑ Fraser AS (1958). "Monte Carlo analyses of genetic models". Nature. 181 (4603): 208–9. doi:10.1038/181208a0. PMID 13504138.
